数据挖掘(七) DBSCAN聚类算法
数据挖掘(七) DBSCAN聚类算法
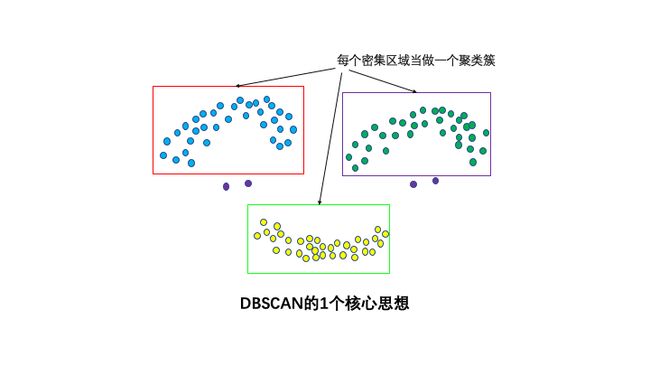
DBSCAN是一种非常著名的基于密度的聚类算法。其英文全称是 Density-Based Spatial Clustering of Applications with Noise,意即:一种基于密度,对噪声鲁棒的空间聚类算法。直观效果上看,DBSCAN算法可以找到样本点的全部密集区域,并把这些密集区域当做一个一个的聚类簇。
基于密度的簇是密度相连的点的集合
DBSCAN算法具有以下特点:
-
基于密度,对远离密度核心的噪声点鲁棒
-
无需知道聚类簇的数量
-
可以发现任意形状的聚类簇
DBSCAN通常适合于对较低维度数据进行聚类分析。
1.基本概念
DBSCAN的基本概念可以用1,2,3,4来总结。
1个核心思想:基于密度。直观效果上看,DBSCAN算法可以找到样本点的全部密集区域,并把这些密集区域当做一个一个的聚类簇。
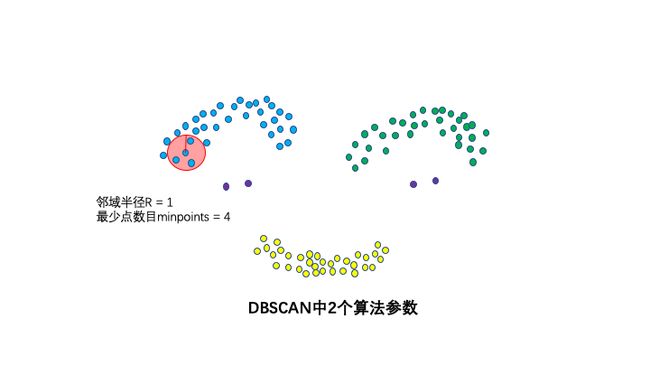
2个算法参数:邻域半径R和最少点数目MinPoints。这两个算法参数实际可以刻画什么叫密集:当邻域半径R内的点的个数大于最少点数目R时,就是密集。
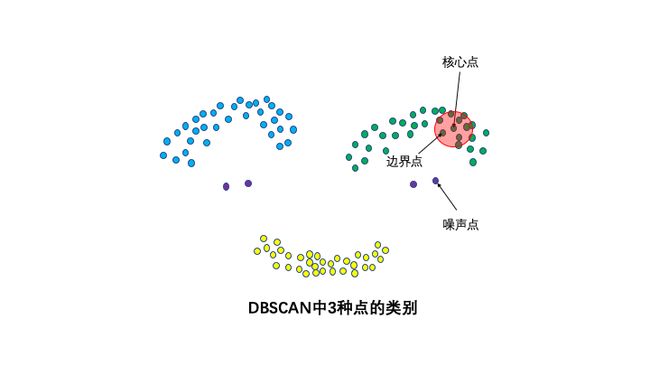
3种点的类别:核心点,边界点和噪声点。邻域半径R内样本点的数量大于等于minpoints的点叫做核心点。不属于核心点但在某个核心点的邻域内的点叫做边界点。既不是核心点也不是边界点的是噪声点。
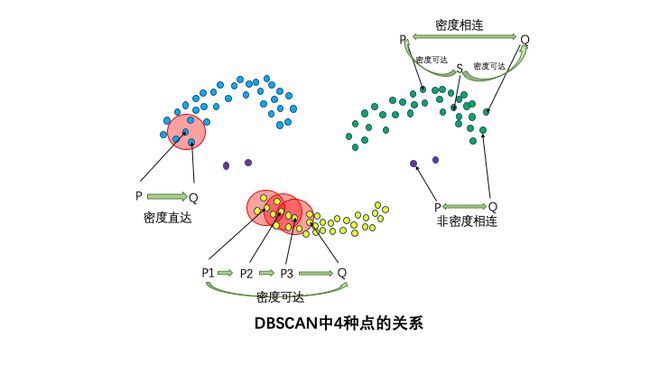
4种点的关系:密度直达,密度可达,密度相连,非密度相连。
如果P为核心点,Q在P的R邻域内,那么称P到Q密度直达。任何核心点到其自身密度直达,密度直达不具有对称性,如果P到Q密度可达,那么Q到P不一定密度可达。
如果存在核心点P2,P3,……,Pn,且P1到P2密度直达,P2到P3密度直达,……,P(n-1)到Pn密度直达,Pn到Q密度直达,则P1到Q密度可达。密度可达也不具有对称性。
如果存在核心点S,使得S到P和Q都密度可达,则P和Q密度相连。密度相连具有对称性,如果P和Q密度相连,那么Q和P也一定密度相连。密度相连的两个点属于同一个聚类簇。
如果两个点不属于密度相连关系,则两个点非密度相连。非密度相连的两个点属于不同的聚类簇,或者其中存在噪声点。
2.算法步骤
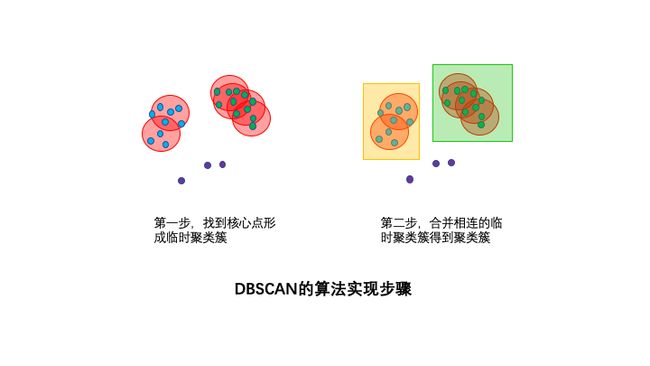
DBSCAN的算法步骤分成两步。
1,寻找核心点形成临时聚类簇。
扫描全部样本点,如果某个样本点R半径范围内点数目>=MinPoints,则将其纳入核心点列表,并将其密度直达的点形成对应的临时聚类簇。
2,合并临时聚类簇得到聚类簇。
对于每一个临时聚类簇,检查其中的点是否为核心点,如果是,将该点对应的临时聚类簇和当前临时聚类簇合并,得到新的临时聚类簇。
重复此操作,直到当前临时聚类簇中的每一个点要么不在核心点列表,要么其密度直达的点都已经在该临时聚类簇,该临时聚类簇升级成为聚类簇。
继续对剩余的临时聚类簇进行相同的合并操作,直到全部临时聚类簇被处理。
3.实验
# 1. 寻找核心点形成临时聚类簇。
# 扫描全部样本点,如果某个样本点R半径范围内点数目>=MinPoints,则将其纳入核心点列表,并将其密度直达的点形成对应的临时聚类簇。
# 2,合并临时聚类簇得到聚类簇。
# 对于每一个临时聚类簇,检查其中的点是否为核心点,如果是,将该点对应的临时聚类簇和当前临时聚类簇合并,得到新的临时聚类簇。
# 重复此操作,直到当前临时聚类簇中的每一个点要么不在核心点列表,要么其密度直达的点都已经在该临时聚类簇,该临时聚类簇升级成为聚类簇。
# 继续对剩余的临时聚类簇进行相同的合并操作,直到全部临时聚类簇被处理。
class DBscan:
def __init__(self,eps,MinPts):
self.eps = eps
self.MinPts = MinPts
# 返回样本点eps半径范围内的索引
def regionQuery(self,i,x):
# 计算当前点与其他所有点的距离
diff = i - x
distances = np.sqrt(np.square(diff).sum(axis=1))
#返回满足邻域点的索引
return list(np.where(distances <= self.eps)[0])
def fit(self,x):
#初始标签为-1
label = -1
m =len(x)
#初始化所有样本点所属的类别,定为-1
cluster = [-1 for i in range(m)]
#已访问样本点
visited = []
for p in range(m): # 遍历每个点
if p not in visited: # 如果没有访问过则执行
NeighborPts = self.regionQuery(x[p],x) # NeighborPts是p的领域点
'''1. 寻找核心点形成临时聚类簇。'''
if len(NeighborPts) < self.MinPts: # 半径范围内点数目 < MinPoints,跳过
#默认标记为-1,后面可能会被加入到其他的邻域内,成为一个密度可达点
continue
else: # 半径范围内点数目>=MinPoints,即当前点为核心点
label += 1
cluster[p] = label
'''2,合并临时聚类簇得到聚类簇。'''
#列表NeighborPts是动态变化的,添加没有访问过的全部密度可达点,划分到一个簇
for p_1 in NeighborPts: # 对核心点的领域点(即临时聚类簇)操作
if p_1 not in visited:
visited.append(p_1) # 标记访问
Ner_NeighborPts = self.regionQuery(x[p_1],x) # 返回每个领域点半径范围内的点
if len(Ner_NeighborPts) >= self.MinPts: # 检查每个领域点半径范围内的点是否满足数量要求
for a in Ner_NeighborPts: # 满足则将这些领域范围内的点加入NeighborPts
if a not in NeighborPts:
NeighborPts.append(a) #使得NeighborPts一直更新,下次检查领域范围内的点的领域点是否满足要求,一直扩张,直到无法扩张
#同时把p_1的类别改为label
cluster[p_1] = label
return cluster
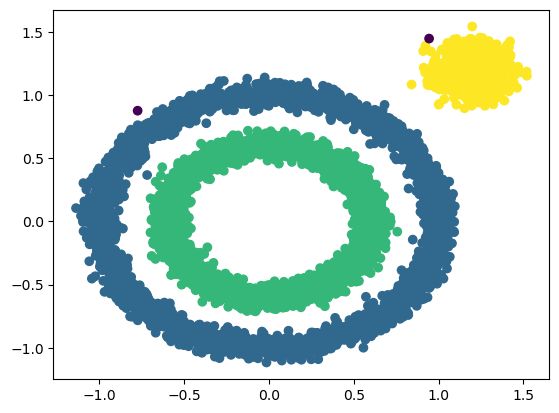
x1,y1 = make_circles(n_samples=5000,factor=0.6,noise=0.05,random_state=2020)
x2,y2 = make_blobs(n_samples=1000,n_features=2,centers=[[1.2,1.2]],cluster_std=0.1,random_state=9)
x1 = np.concatenate((x1,x2))
Dbscan =DBscan(eps=0.1,MinPts=10)
y_pred = Dbscan.fit(x1)
plt.scatter(x1[:,0],x1[:,1],c=y_pred,marker='o')
plt.show()
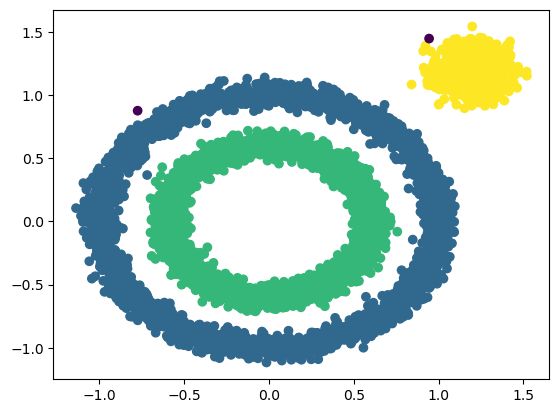
model = DBSCAN(eps=0.1,min_samples=10)
y_preds = model.fit_predict(x1)
plt.scatter(x1[:,0],x1[:,1],c=y_preds,marker='o')
plt.show()
刚才验证大数据集时,为什么sklearn速度比较快,是因为:
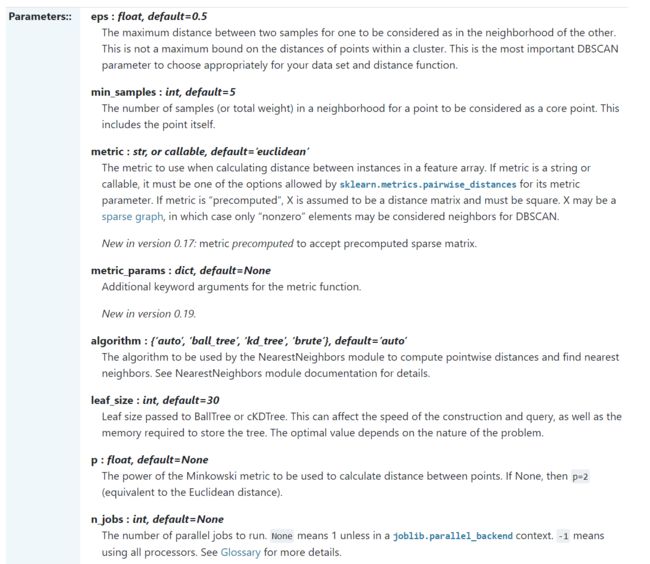
参数‘“algorithm”,算法一共有三种,第一种是蛮力实现,第二种是KD树实现,第三种是球树实现。K近邻法(KNN)中也是这样,一共有4种可选输入,‘brute’对应蛮力实现,也就是我们这种,‘kd_tree’对应第二种KD树实现,‘ball_tree’对应第三种的球树实现, ‘auto’则会在上面三种算法中做权衡,选择一个拟合最好的最优算法。需要注意的是,如果输入样本特征是稀疏的时候,无论我们选择哪种算法,最后scikit-learn都会去用蛮力实现‘brute’。
默认的距离也是欧氏距离。
和传统的K-Means算法相比,DBSCAN最大的不同就是不需要输入类别数k,当然它最大的优势是可以发现任意形状的聚类簇,而不是像K-Means,一般仅仅使用于凸的样本集聚类。同时它在聚类的同时还可以找出异常点,这点和BIRCH算法类似。
那么我们什么时候需要用DBSCAN来聚类呢?一般来说,如果数据集是稠密的,并且数据集不是凸的,那么用DBSCAN会比K-Means聚类效果好很多。如果数据集不是稠密的,则不推荐用DBSCAN来聚类。
下面对DBSCAN算法的优缺点做一个总结。
DBSCAN的主要优点有:
1) 可以对任意形状的稠密数据集进行聚类,相对的,K-Means之类的聚类算法一般只适用于凸数据集。
2) 可以在聚类的同时发现异常点,对数据集中的异常点不敏感。
3) 聚类结果没有偏倚,相对的,K-Means之类的聚类算法初始值对聚类结果有很大影响。
DBSCAN的主要缺点有:
1)如果样本集的密度不均匀、聚类间距差相差很大时,聚类质量较差,这时用DBSCAN聚类一般不适合。
2) 如果样本集较大时,聚类收敛时间较长,此时可以对搜索最近邻时建立的KD树或者球树进行规模限制来改进。
3)
调参相对于传统的K-Means之类的聚类算法稍复杂,主要需要对距离阈值ϵ,邻域样本数阈值MinPts联合调参,不同的参数组合对最后的聚类效果有较大影响。