基于k-means实现鸢尾花聚类
基于k-means实现鸢尾花聚类
- K-means (k均值聚类)
- 手动实现
- 基于sklearn实现鸢尾花聚类
K-means (k均值聚类)
与有监督学习相比,无监督学习的样本没有任何标记。无监督学习的算法需要自动找到这些没有标记的数据里面的数据结构和特征。
聚类:把数据集分成一个个的簇( cluster )

使用K-means聚类算法筛实现鸢尾花聚类
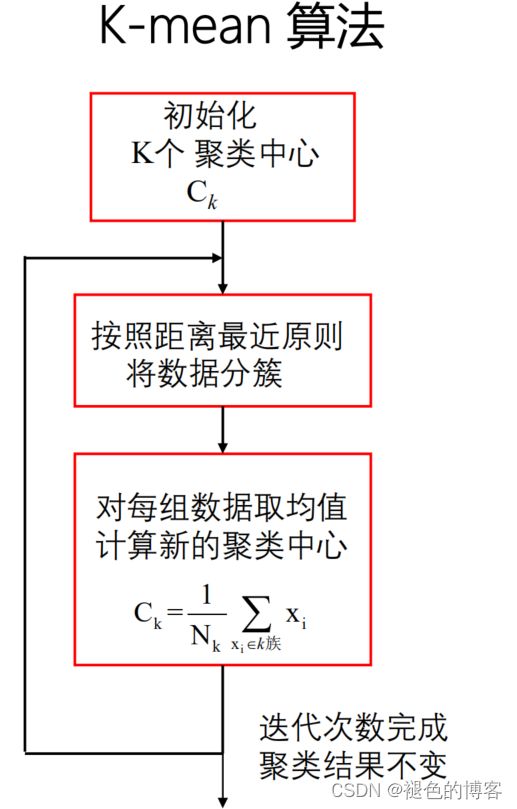
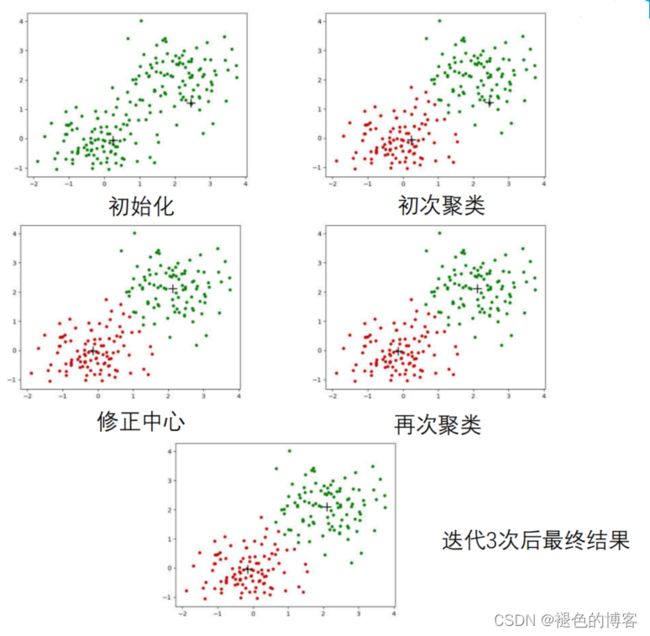
对于给定的样本集,按照样本之间的距离大小,将样本集划分为K个簇,让簇内的点尽量紧密的连在一起,而让簇间的距离尽量的大
手动实现
鸢尾花数据集描述
1、包含3种类型数据集,共150条数据 ;
2、包含4项特征:花萼长度、花萼宽度、花瓣长度、花瓣宽度
# 法一:直接手写实现
# 欧氏距离计算
def distEclud(x,y):
return np.sqrt(np.sum((x-y)**2)) # 计算欧氏距离
# 为给定数据集构建一个包含K个随机质心centroids的集合
def randCent(dataSet,k):
m,n = dataSet.shape #m=150,n=4
centroids = np.zeros((k,n)) #4*4
for i in range(k): # 执行四次
index = int(np.random.uniform(0,m)) # 产生0到150的随机数(在数据集中随机挑一个向量做为质心的初值)
centroids[i,:] = dataSet[index,:] #把对应行的四个维度传给质心的集合
return centroids
# k均值聚类算法
def KMeans(dataSet,k):
m = np.shape(dataSet)[0] #行数150
# 第一列存每个样本属于哪一簇(四个簇)
# 第二列存每个样本的到簇的中心点的误差
clusterAssment = np.mat(np.zeros((m,2)))# .mat()创建150*2的矩阵
clusterChange = True
# 1.初始化质心centroids
centroids = randCent(dataSet,k)#4*4
while clusterChange:
# 样本所属簇不再更新时停止迭代
clusterChange = False
# 遍历所有的样本(行数150)
for i in range(m):
minDist = 100000.0
minIndex = -1
# 遍历所有的质心
#2.找出最近的质心
for j in range(k):
# 计算该样本到4个质心的欧式距离,找到距离最近的那个质心minIndex
distance = distEclud(centroids[j,:],dataSet[i,:])
if distance < minDist:
minDist = distance
minIndex = j
# 3.更新该行样本所属的簇
if clusterAssment[i,0] != minIndex:
clusterChange = True
clusterAssment[i,:] = minIndex,minDist**2
#4.更新质心
for j in range(k):
# np.nonzero(x)返回值不为零的元素的下标,它的返回值是一个长度为x.ndim(x的轴数)的元组
# 元组的每个元素都是一个整数数组,其值为非零元素的下标在对应轴上的值。
# 矩阵名.A 代表将 矩阵转化为array数组类型
# 这里取矩阵clusterAssment所有行的第一列,转为一个array数组,与j(簇类标签值)比较,返回true or false
# 通过np.nonzero产生一个array,其中是对应簇类所有的点的下标值(x个)
# 再用这些下标值求出dataSet数据集中的对应行,保存为pointsInCluster(x*4)
pointsInCluster = dataSet[np.nonzero(clusterAssment[:,0].A == j)[0]] # 获取对应簇类所有的点(x*4)
centroids[j,:] = np.mean(pointsInCluster,axis=0) # 求均值,产生新的质心
# axis=0,那么输出是1行4列,求的是pointsInCluster每一列的平均值,即axis是几,那就表明哪一维度被压缩成1
print("cluster complete")
return centroids,clusterAssment
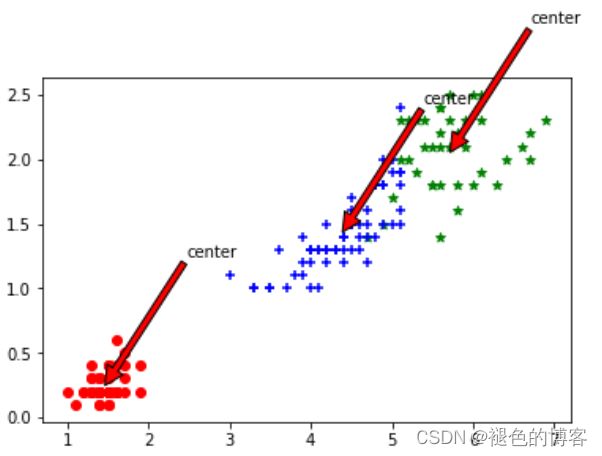
def draw(data,center,assment):
length=len(center)
fig=plt.figure
data1=data[np.nonzero(assment[:,0].A == 0)[0]]
data2=data[np.nonzero(assment[:,0].A == 1)[0]]
data3=data[np.nonzero(assment[:,0].A == 2)[0]]
# 选取前两个维度绘制原始数据的散点图
plt.scatter(data1[:,0],data1[:,1],c="red",marker='o',label='label0')
plt.scatter(data2[:,0],data2[:,1],c="green", marker='*', label='label1')
plt.scatter(data3[:,0],data3[:,1],c="blue", marker='+', label='label2')
# 绘制簇的质心点
for i in range(length):
plt.annotate('center',xy=(center[i,0],center[i,1]),xytext=\
(center[i,0]+1,center[i,1]+1),arrowprops=dict(facecolor='yellow'))
# plt.annotate('center',xy=(center[i,0],center[i,1]),xytext=\
# (center[i,0]+1,center[i,1]+1),arrowprops=dict(facecolor='red'))
plt.show()
# 选取后两个维度绘制原始数据的散点图
plt.scatter(data1[:,2],data1[:,3],c="red",marker='o',label='label0')
plt.scatter(data2[:,2],data2[:,3],c="green", marker='*', label='label1')
plt.scatter(data3[:,2],data3[:,3],c="blue", marker='+', label='label2')
# 绘制簇的质心点
for i in range(length):
plt.annotate('center',xy=(center[i,2],center[i,3]),xytext=\
(center[i,2]+1,center[i,3]+1),arrowprops=dict(facecolor='yellow'))
plt.show()
调用函数查看效果
dataSet = X
k = 3
centroids,clusterAssment = KMeans(dataSet,k)
draw(dataSet,centroids,clusterAssment)
基于sklearn实现鸢尾花聚类
导入相关包
import matplotlib.pyplot as plt
import numpy as np
from sklearn.cluster import KMeans
from sklearn import datasets
直接从sklearn.datasets中加载数据集
# 直接从sklearn中获取数据集
iris = datasets.load_iris()
X = iris.data[:, :4] # 表示我们取特征空间中的4个维度
print(X.shape)
绘制二维数据分布图
每个样本使用两个特征,绘制其二维数据分布图
# 取前两个维度(萼片长度、萼片宽度),绘制数据分布图
plt.scatter(X[:, 0], X[:, 1], c="red", marker='o', label='see')
plt.xlabel('sepal length')
plt.ylabel('sepal width')
plt.legend(loc=2)
plt.show()
def Model(n_clusters):
estimator = KMeans(n_clusters=n_clusters)# 构造聚类器
return estimator
def train(estimator):
estimator.fit(X) # 聚类
训练
# 初始化实例,并开启训练拟合
estimator=Model(3)
train(estimator)
可视化展示
label_pred = estimator.labels_ # 获取聚类标签
# 绘制k-means结果
x0 = X[label_pred == 0]
x1 = X[label_pred == 1]
x2 = X[label_pred == 2]
plt.scatter(x0[:, 0], x0[:, 1], c="red", marker='o', label='label0')
plt.scatter(x1[:, 0], x1[:, 1], c="green", marker='*', label='label1')
plt.scatter(x2[:, 0], x2[:, 1], c="blue", marker='+', label='label2')
plt.xlabel('sepal length')
plt.ylabel('sepal width')
plt.legend(loc=2)
plt.show()