- 程序人生:技术人如何实现职业阶梯的跨越式发展
AI天才研究院
AI大模型企业级应用开发实战AgenticAI实战AI人工智能与大数据程序人生职场和发展ai
程序人生:技术人如何实现职业阶梯的跨越式发展关键词:职业发展、技术领导力、T型人才、职业规划、跨领域能力、持续学习、技术管理摘要:本文针对技术从业者的职业发展痛点,构建了系统化的职业阶梯跨越模型。通过解析技术人才成长的核心阶段与能力模型,结合数学量化评估体系和实战案例,提供从技术深耕到领导力跃迁的完整路径。内容涵盖能力矩阵构建、项目实战策略、跨领域知识融合、个人品牌经营等关键模块,帮助技术人突破职
- 程序人生职业生涯学习成长,学历提升是秘诀?
AI天才研究院
AI大模型企业级应用开发实战AgenticAI实战AI人工智能与大数据程序人生学习职场和发展ai
程序人生职业生涯学习成长,学历提升是秘诀?关键词:程序员职业发展、学历提升、持续学习、技术能力、职业规划、终身学习、技能提升摘要:本文深入探讨程序员职业生涯中的学习成长路径,分析学历提升在职业发展中的实际作用。通过对比不同发展阶段的技术能力需求与学历要求,揭示程序员职业成长的核心要素。文章将提供系统化的学习框架、实用的技能提升策略,以及平衡学历教育与实战经验的方法论,帮助程序员在快速变化的技术行业
- 【Java实现AI抽奖解签系统:24签个性化运势解读】
王大师王文峰
java开发语言
本人详解作者:王文峰,参加过CSDN2020年度博客之星,《Java王大师王天师》公众号:JAVA开发王大师,专注于天道酬勤的Java开发问题中国国学、传统文化和代码爱好者的程序人生,期待你的关注和支持!本人外号:神秘小峯山峯转载说明:务必注明来源(注明:作者:王文峰哦)【Java实现AI抽奖解签系统:24签个性化运势解读】学习教程(传送门)Java实现AI抽奖解签系统:24签个性化运势解读系统设
- Java时间日期处理全攻略:多种写法、计算与获取方法
王大师王文峰
java开发语言
本人详解作者:王文峰,参加过CSDN2020年度博客之星,《Java王大师王天师》公众号:JAVA开发王大师,专注于天道酬勤的Java开发问题中国国学、传统文化和代码爱好者的程序人生,期待你的关注和支持!本人外号:神秘小峯山峯转载说明:务必注明来源(注明:作者:王文峰哦)Java时间日期处理全攻略:多种写法、计算与获取方法学习教程(传送门)Java时间日期处理全攻略:多种写法、计算与获取方法**一
- C#初学者指南:从零开始掌握基础语法
王大师王文峰
c#开发语言
本人详解作者:王文峰,参加过CSDN2020年度博客之星,《Java王大师王天师》公众号:JAVA开发王大师,专注于天道酬勤的Java开发问题中国国学、传统文化和代码爱好者的程序人生,期待你的关注和支持!本人外号:神秘小峯山峯转载说明:务必注明来源(注明:作者:王文峰哦)C#初学者指南:从零开始掌握基础语法学习教程(传送门)C#初学者指南:从零开始掌握基础语法环境搭建:准备你的第一个C#项目C#基
- 直击2025 C#架构师面试:分布式库存/大模型集成/热更新配置等企业级场景深度解析(含答案+性能优化技巧)
王大师王文峰
c#面试分布式
本人详解作者:王文峰,参加过CSDN2020年度博客之星,《Java王大师王天师》公众号:JAVA开发王大师,专注于天道酬勤的Java开发问题中国国学、传统文化和代码爱好者的程序人生,期待你的关注和支持!本人外号:神秘小峯山峯转载说明:务必注明来源(注明:作者:王文峰哦)直击2025C#架构师面试:分布式库存/大模型集成/热更新配置等企业级场景深度解析(含答案+性能优化技巧)学习教程(传送门)20
- 服务+货物混合合同订单的技术实现与结算逻辑(Java版)
王大师王文峰
java开发语言
本人详解作者:王文峰,参加过CSDN2020年度博客之星,《Java王大师王天师》公众号:JAVA开发王大师,专注于天道酬勤的Java开发问题中国国学、传统文化和代码爱好者的程序人生,期待你的关注和支持!本人外号:神秘小峯山峯转载说明:务必注明来源(注明:作者:王文峰哦)服务+货物混合合同订单的技术实现与结算逻辑(Java版)学习教程(传送门)服务+货物混合合同订单的技术实现与结算逻辑(Java版
- 程序人生如何在技术会议中收获学习与成长
AI天才研究院
计算AI大模型企业级应用开发实战AI人工智能与大数据程序人生学习职场和发展ai
程序人生:如何在技术会议中收获学习与成长关键词:技术会议、开发者成长、参会策略、知识获取、人脉拓展、职业发展、技术洞察摘要:技术会议是程序员提升技术视野、获取前沿知识、拓展职业网络的重要平台。本文从参会前的战略规划、参会中的高效吸收、会后的持续转化三个维度,系统解析如何通过科学的参会策略实现能力跃升。结合具体案例、工具方法和实战经验,阐述技术会议在职业发展中的杠杆作用,帮助开发者将会议价值最大化,
- 程序人生:腾讯面试背后的职业生涯学习与成长秘籍
AI天才研究院
程序人生面试学习ai
程序人生:腾讯面试背后的职业生涯学习与成长秘籍关键词:腾讯面试、技术深度、工程能力、系统思维、职业成长、软技能、刻意练习摘要:本文以腾讯面试为切入点,拆解顶级互联网公司对技术人才的核心考察逻辑,结合真实面试案例与程序员职业生涯发展阶段,总结“技术深度-工程能力-系统思维-软技能”四维成长模型。通过生活化的比喻、具体的面试场景还原与可落地的成长方法论,帮助开发者从“应对面试”升级为“终身成长”,找到
- 程序人生职业生涯,学习成长为薪酬谈判添砖加瓦
ChatGPTAI大模型应用入门实战与进阶程序人生学习微信小程序ai
程序人生职业生涯:学习成长为薪酬谈判添砖加瓦关键词:程序员职业生涯、技术能力体系、薪酬谈判策略、职业成长模型、市场价值评估、学习路径规划、胜任力模型摘要:本文针对程序员群体,构建"学习成长-能力提升-薪酬谈判"的完整逻辑链条。通过解析技术人员职业发展的三阶段模型,建立包含硬技能/软技能/项目经验的三维能力评估体系,提供可量化的学习效果评估方法与薪酬谈判实战策略。结合Python代码实现能力自评工具
- 当 AI 能写代码修 bug,高考填报计算机专业是“火坑”还是“新机遇” |深度对话 6 位专家
CSDN 程序人生
人工智能bug高考
作者|梦依丹出品丨CSDN程序人生一年一度的高考如期而至,今年,将有1335万名考生踏入考场,如果说考试是考生的战场,那么让无数家庭真正反复权衡、难以抉择的,其实是考后的另一道大题——「填什么专业」。从“高考志愿填报导师”张雪峰推出的17999元的高考志愿填报服务不到3分钟便被抢购一空可见有多火,而计算机和人工智能更是他经常推荐的专业。今年,在AI浪潮的席卷之下,这道选择题更添了几分迷思与变数:当
- 哈工大计算机系统大作业——程序人生-Hello’s P2P
m0_72541769
课程设计
计算机系统大作业题目程序人生-Hello’sP2P专业信息安全学号2022112864班级2203201学生xxx指导教师史先俊计算机科学与技术学院2024年5月摘要本论文旨在详细探讨计算机系统中程序从源码到可执行文件的整个转换过程,具体分析了C语言程序`Hello.c`的编译、链接、运行等各个阶段。通过使用GCC编译器以及Ubuntu环境下的一系列工具,本文对预处理、编译、汇编、链接、加载和运行
- 哈工大计统大作业-hello的一生
YX030212
课程设计p2p网络
计算机系统大作业题目程序人生-Hello’sP2P专业人工智能学号2021113560班级WL026学生陈禹西指导教师吴锐计算机科学与技术学院2023年5月摘要本文以一个简单的hello.c程序开始,介绍了一个程序在Linux下运行的完整生命周期,包括预处理、编译、汇编、链接、进程管理、存储管理、I/O管理这几部分,一步步详细介绍了程序从被键盘输入、保存到磁盘,直到最后程序运行结束,程序变为僵尸进
- 2025年春哈工大计算机系统(CSAPP)课程大作业:程序人生
The_Skynet
CSAPP期末大作业
通过这个大作业稍微复习了一下课程知识,这只是按课程要求在这里发布的。我把文件的链接贴在这里了:https://github.com/Trappist-1st/HIT-CSAPP-big_homework
- 《深入理解计算机系统》期末大作业:程序人生-Hello’s P2P
Reisen_Inaba
摘要输出Hello,world的程序,是所有人编程学习的第一步,也是最简单的程序。本文将以程序hello.c为例,分析一个具有一般性的程序在Linux环境下,从预处理到编译、汇编、链接等的完整过程。综合《计算机系统基础》科目所学,考察程序的生命周期,并分析程序作为进程,与内存及外部IO设备的交互过程。关键词:系统,周期,程序生成,进程,交互目录第1章概述......................
- 解锁程序人生学习成长密码,从目标设定开始
AI天才研究院
ChatGPTAI大模型应用入门实战与进阶程序人生学习微信小程序ai
解锁程序人生学习成长密码,从目标设定开始关键词:程序员成长、目标设定、学习路径、技能提升、职业规划、刻意练习、反馈机制摘要:本文深入探讨程序员如何通过科学的目标设定方法实现职业成长。文章从目标设定的重要性出发,详细介绍了SMART原则、OKR方法等技术,并结合程序员职业特点,提供了可操作的学习路径规划、技能提升策略和反馈机制建立方法。通过实际案例和工具推荐,帮助程序员构建系统化的成长体系,实现从初
- Stable Diffusion 2025新手全套安装教程 零基础小白一键解锁AI绘图神器,轻松玩转AI绘画
AI设计酷卡
stablediffusion人工智能AI作画AIGC
我们今天不谈编程,也不谈程序人生,就来唠一唠AI绘图~~StableDiffusion是什么♥️StableDiffusion,简称SD,是一种基于深度学习的图像处理技术!它属于称之为扩散模型diffusionmodel的深度学习AI,是生成模型的一种!这意味着SD的核心作用就是生成类似于其训练数据的新数据,对于SD来说,这个数据就是(图像)图片简单的说StableDiffusion就是一种使用A
- 程序人生:远程工作环境下的技术成长与职业发展
AI天才研究院
ChatGPTAI大模型企业级应用开发实战程序人生远程工作网络ai
程序人生:远程工作环境下的技术成长与职业发展关键词:远程工作、技术成长、职业发展、程序员、协作工具、时间管理、自我驱动摘要:本文深入探讨了在远程工作环境下程序员如何实现技术成长与职业发展的策略和方法。文章从远程工作的特点出发,分析了技术成长的挑战与机遇,提出了系统化的解决方案,包括高效学习路径、技术栈规划、远程协作技巧、职业发展策略等核心内容。通过实际案例、工具推荐和具体实施步骤,为程序员在远程工
- 程序人生进阶指南:掌握这5种跨学科思维让你脱颖而出
程序人生职场和发展ai
程序人生进阶指南:掌握这5种跨学科思维让你脱颖而出关键词:程序员成长、跨学科思维、系统思维、设计思维、经济学思维、心理学思维、数学思维摘要:本文探讨了程序员如何通过培养5种关键跨学科思维(系统思维、设计思维、经济学思维、心理学思维和数学思维)实现职业突破。文章详细解析了每种思维的核心概念、应用场景和在编程中的具体实践方法,帮助技术人员拓宽视野、提升问题解决能力,最终在职业生涯中脱颖而出。1.背景介
- 程序人生--2005年(30)
chilavert318
程序人生涉世之初软件生涯经历
82搬家年底我又一次的搬家了,工作5年了我搬过2次家,一次是藩后街,另一次是丝茅冲。而这次的意义不同,因为这个家是指真正意义上的家!很有归宿感和成就感!在公司单身宿舍生活了3年,其实这里条件真的还不错。有热水、有空调、有电视、可以上网,理想上的职业宿舍,他都具备了。可是总觉得他还缺少些什么,后来细细想想他总归不是属于自己的东西,他只是我生活旅途的一个小站,条件再好我也会离开这里的。搬家工作是在年底
- 学习型组织,让程序人生职业生涯学习成长不再迷茫
AI大模型应用之禅
程序人生学习职场和发展ai
学习型组织,让程序人生职业生涯学习成长不再迷茫关键词:学习型组织、程序员成长、职业发展、团队学习、个人-组织共进化摘要:本文从程序员职业发展的典型迷茫出发,结合"学习型组织"这一管理科学经典理论,用程序员熟悉的技术思维拆解其核心逻辑。通过"技术团队如何从’代码作坊’升级为’学习引擎’"的实战案例,讲解学习型组织的五大核心要素(自我超越、心智模式、共同愿景、团队学习、系统思考)如何具体落地,帮助程序
- 程序人生:自我驱动下的职业生涯学习与成长之路
AI天才研究院
计算AI大模型应用入门实战与进阶程序人生学习职场和发展ai
程序人生:自我驱动下的职业生涯学习与成长之路关键词:程序人生、自我驱动、职业生涯、学习成长、技术发展摘要:本文聚焦于程序员在职业生涯中的学习与成长,强调自我驱动的重要性。通过对程序人生的多维度剖析,阐述了程序员职业生涯的不同阶段特点、学习的核心概念与方法、关键算法原理及实际操作步骤、数学模型在编程中的应用、项目实战案例、实际应用场景等内容。同时推荐了相关的工具和资源,分析了未来发展趋势与挑战,并对
- 【提升开发效率的秘密武器:IntelliJ IDEA 插件完全使用指南】依赖冲突检测,保存时自动优化代码,编译时智能错误修复
王大师王文峰
编程利器IDEAintellij-ideajavaide
本人详解作者:王文峰,参加过CSDN2020年度博客之星,《Java王大师王天师》公众号:JAVA开发王大师,专注于天道酬勤的Java开发问题中国国学、传统文化和代码爱好者的程序人生,期待你的关注和支持!本人外号:神秘小峯山峯转载说明:务必注明来源(注明:作者:王文峰哦)【提升开发效率的秘密武器:IntelliJIDEA插件完全使用指南】依赖冲突检测,保存时自动优化代码,编译时智能错误修复学习教程
- 【Python绘制创意爱心代码】多种技术手段实现动态、立体、交互式爱心效果,展示Python在创意编程中的技术魅力。所有代码可直接运行,需Python 3.6+环境。
王大师王文峰
python开发语言
本人详解作者:王文峰,参加过CSDN2020年度博客之星,《Java王大师王天师》公众号:JAVA开发王大师,专注于天道酬勤的Java开发问题中国国学、传统文化和代码爱好者的程序人生,期待你的关注和支持!本人外号:神秘小峯山峯转载说明:务必注明来源(注明:作者:王文峰哦)【Python绘制创意爱心代码】多种技术手段实现动态、立体、交互式爱心效果,展示Python在创意编程中的技术魅力。所有代码可直
- React中useEffect和useLayoutEffect的区别
CreatorRay
前端面试reactreact.js前端面试
在最近一次面试中被问到,我印象中好像从来没用过useLayoutEffect,就没答上来。但是看名字应该是跟布局相关的,而且跟useEffect会有类似的作用。在React中,useEffect和useLayoutEffect都是用于处理副作用的Hooks,但它们的执行时机和对渲染流程的影响有显著区别。以下是两者的核心差异及使用场景:公众号:Code程序人生,个人网站:https://creato
- 【程序人生】中年技术女性,什么是生活的重点?
JosieBook
程序人生生活职场和发展
文章目录⭐前言⭐一、明确“成功”的定义:先破后立警惕社会规训:价值观排序工具:⭐二、怎职业发展:聚焦长板,打造不可替代性30岁职场破局策略:职场可见度提升:⭐三、人际关系:构建支持系统关系断舍离:亲密关系选择:⭐四、身心健康:可持续成功的根基身体管理:情绪调节:⭐五、财务安全:抵御风险的核心防线30岁财务健康标准:投资优先级:⭐六、财务安长期主义:制定“3年跃迁计划”目标锚定法:复盘与迭代:⭐关键
- JAVA从万级QPS到亿级吞吐,如何用非阻塞模型突破传统架构的性能瓶颈
王大师王文峰
java架构开发语言
本人详解作者:王文峰,参加过CSDN2020年度博客之星,《Java王大师王天师》公众号:JAVA开发王大师,专注于天道酬勤的Java开发问题中国国学、传统文化和代码爱好者的程序人生,期待你的关注和支持!本人外号:神秘小峯山峯转载说明:务必注明来源(注明:作者:王文峰哦)JAVA从万级QPS到亿级吞吐,如何用非阻塞模型突破传统架构的性能瓶颈学习教程(传送门)引言:当线程池成为瓶颈——某视频平台春节
- 【C#】VS2019怎么能无论是Debug还是Release模式,生成路径都在Release文件夹下?
JosieBook
#C#语言vs
文章目录⭐问题⭐解决标题详情作者JosieBook头衔CSDN博客专家资格、阿里云社区专家博主、软件设计工程师博客内容开源、框架、软件工程、全栈(,NET/Java/Python/C++)、数据库、操作系统、大数据、人工智能、工控、网络、程序人生口号Tobeyourself,todowhatyouwant.联系方式q:1967473153欢迎三连点赞、✍评论、⭐收藏⭐问题正常情况下,是这样:怎么让
- 深挖JVM隐藏优化点与百万QPS系统调优【突破认知:JVM内存管理的9大反直觉真相】通过三个违背‘常识‘的调优策略,将GC停顿时间从1.2秒降至80ms,节省40%服务器成本
王大师王文峰
jvm服务器运维
本人详解作者:王文峰,参加过CSDN2020年度博客之星,《Java王大师王天师》公众号:JAVA开发王大师,专注于天道酬勤的Java开发问题中国国学、传统文化和代码爱好者的程序人生,期待你的关注和支持!本人外号:神秘小峯山峯转载说明:务必注明来源(注明:作者:王文峰哦)深挖JVM隐藏优化点与百万QPS系统调优【突破认知:JVM内存管理的9大反直觉真相】通过三个违背'常识'的调优策略,将GC停顿时
- Vue 技术博客:从零开始构建一个 Vue Markdown 编辑器
王大师王文峰
Java基础到框架vue.js编辑器前端
本人详解作者:王文峰,参加过CSDN2020年度博客之星,《Java王大师王天师》公众号:JAVA开发王大师,专注于天道酬勤的Java开发问题中国国学、传统文化和代码爱好者的程序人生,期待你的关注和支持!本人外号:神秘小峯山峯转载说明:务必注明来源(注明:作者:王文峰哦)学习教程(传送门)Vue技术博客:从零开始构建一个VueMarkdown编辑器前言环境准备实现步骤1.引入组件与库2.模板设计3
- Js函数返回值
_wy_
jsreturn
一、返回控制与函数结果,语法为:return 表达式;作用: 结束函数执行,返回调用函数,而且把表达式的值作为函数的结果 二、返回控制语法为:return;作用: 结束函数执行,返回调用函数,而且把undefined作为函数的结果 在大多数情况下,为事件处理函数返回false,可以防止默认的事件行为.例如,默认情况下点击一个<a>元素,页面会跳转到该元素href属性
- MySQL 的 char 与 varchar
bylijinnan
mysql
今天发现,create table 时,MySQL 4.1有时会把 char 自动转换成 varchar
测试举例:
CREATE TABLE `varcharLessThan4` (
`lastName` varchar(3)
) ;
mysql> desc varcharLessThan4;
+----------+---------+------+-
- Quartz——TriggerListener和JobListener
eksliang
TriggerListenerJobListenerquartz
转载请出自出处:http://eksliang.iteye.com/blog/2208624 一.概述
listener是一个监听器对象,用于监听scheduler中发生的事件,然后执行相应的操作;你可能已经猜到了,TriggerListeners接受与trigger相关的事件,JobListeners接受与jobs相关的事件。
二.JobListener监听器
j
- oracle层次查询
18289753290
oracle;层次查询;树查询
.oracle层次查询(connect by)
oracle的emp表中包含了一列mgr指出谁是雇员的经理,由于经理也是雇员,所以经理的信息也存储在emp表中。这样emp表就是一个自引用表,表中的mgr列是一个自引用列,它指向emp表中的empno列,mgr表示一个员工的管理者,
select empno,mgr,ename,sal from e
- 通过反射把map中的属性赋值到实体类bean对象中
酷的飞上天空
javaee泛型类型转换
使用过struts2后感觉最方便的就是这个框架能自动把表单的参数赋值到action里面的对象中
但现在主要使用Spring框架的MVC,虽然也有@ModelAttribute可以使用但是明显感觉不方便。
好吧,那就自己再造一个轮子吧。
原理都知道,就是利用反射进行字段的赋值,下面贴代码
主要类如下:
import java.lang.reflect.Field;
imp
- SAP HANA数据存储:传统硬盘的瓶颈问题
蓝儿唯美
HANA
SAPHANA平台有各种各样的应用场景,这也意味着客户的实施方法有许多种选择,关键是如何挑选最适合他们需求的实施方案。
在 《Implementing SAP HANA》这本书中,介绍了SAP平台在现实场景中的运作原理,并给出了实施建议和成功案例供参考。本系列文章节选自《Implementing SAP HANA》,介绍了行存储和列存储的各自特点,以及SAP HANA的数据存储方式如何提升空间压
- Java Socket 多线程实现文件传输
随便小屋
javasocket
高级操作系统作业,让用Socket实现文件传输,有些代码也是在网上找的,写的不好,如果大家能用就用上。
客户端类:
package edu.logic.client;
import java.io.BufferedInputStream;
import java.io.Buffered
- java初学者路径
aijuans
java
学习Java有没有什么捷径?要想学好Java,首先要知道Java的大致分类。自从Sun推出Java以来,就力图使之无所不包,所以Java发展到现在,按应用来分主要分为三大块:J2SE,J2ME和J2EE,这也就是Sun ONE(Open Net Environment)体系。J2SE就是Java2的标准版,主要用于桌面应用软件的编程;J2ME主要应用于嵌入是系统开发,如手机和PDA的编程;J2EE
- APP推广
aoyouzi
APP推广
一,免费篇
1,APP推荐类网站自主推荐
最美应用、酷安网、DEMO8、木蚂蚁发现频道等,如果产品独特新颖,还能获取最美应用的评测推荐。PS:推荐简单。只要产品有趣好玩,用户会自主分享传播。例如足迹APP在最美应用推荐一次,几天用户暴增将服务器击垮。
2,各大应用商店首发合作
老实盯着排期,多给应用市场官方负责人献殷勤。
3,论坛贴吧推广
百度知道,百度贴吧,猫扑论坛,天涯社区,豆瓣(
- JSP转发与重定向
百合不是茶
jspservletJava Webjsp转发
在servlet和jsp中我们经常需要请求,这时就需要用到转发和重定向;
转发包括;forward和include
例子;forwrad转发; 将请求装法给reg.html页面
关键代码;
req.getRequestDispatcher("reg.html
- web.xml之jsp-config
bijian1013
javaweb.xmlservletjsp-config
1.作用:主要用于设定JSP页面的相关配置。
2.常见定义:
<jsp-config>
<taglib>
<taglib-uri>URI(定义TLD文件的URI,JSP页面的tablib命令可以经由此URI获取到TLD文件)</tablib-uri>
<taglib-location>
TLD文件所在的位置
- JSF2.2 ViewScoped Using CDI
sunjing
CDIJSF 2.2ViewScoped
JSF 2.0 introduced annotation @ViewScoped; A bean annotated with this scope maintained its state as long as the user stays on the same view(reloads or navigation - no intervening views). One problem w
- 【分布式数据一致性二】Zookeeper数据读写一致性
bit1129
zookeeper
很多文档说Zookeeper是强一致性保证,事实不然。关于一致性模型请参考http://bit1129.iteye.com/blog/2155336
Zookeeper的数据同步协议
Zookeeper采用称为Quorum Based Protocol的数据同步协议。假如Zookeeper集群有N台Zookeeper服务器(N通常取奇数,3台能够满足数据可靠性同时
- Java开发笔记
白糖_
java开发
1、Map<key,value>的remove方法只能识别相同类型的key值
Map<Integer,String> map = new HashMap<Integer,String>();
map.put(1,"a");
map.put(2,"b");
map.put(3,"c"
- 图片黑色阴影
bozch
图片
.event{ padding:0; width:460px; min-width: 460px; border:0px solid #e4e4e4; height: 350px; min-heig
- 编程之美-饮料供货-动态规划
bylijinnan
动态规划
import java.util.Arrays;
import java.util.Random;
public class BeverageSupply {
/**
* 编程之美 饮料供货
* 设Opt(V’,i)表示从i到n-1种饮料中,总容量为V’的方案中,满意度之和的最大值。
* 那么递归式就应该是:Opt(V’,i)=max{ k * Hi+Op
- ajax大参数(大数据)提交性能分析
chenbowen00
WebAjax框架浏览器prototype
近期在项目中发现如下一个问题
项目中有个提交现场事件的功能,该功能主要是在web客户端保存现场数据(主要有截屏,终端日志等信息)然后提交到服务器上方便我们分析定位问题。客户在使用该功能的过程中反应点击提交后反应很慢,大概要等10到20秒的时间浏览器才能操作,期间页面不响应事件。
根据客户描述分析了下的代码流程,很简单,主要通过OCX控件截屏,在将前端的日志等文件使用OCX控件打包,在将之转换为
- [宇宙与天文]在太空采矿,在太空建造
comsci
我们在太空进行工业活动...但是不太可能把太空工业产品又运回到地面上进行加工,而一般是在哪里开采,就在哪里加工,太空的微重力环境,可能会使我们的工业产品的制造尺度非常巨大....
地球上制造的最大工业机器是超级油轮和航空母舰,再大些就会遇到困难了,但是在空间船坞中,制造的最大工业机器,可能就没
- ORACLE中CONSTRAINT的四对属性
daizj
oracleCONSTRAINT
ORACLE中CONSTRAINT的四对属性
summary:在data migrate时,某些表的约束总是困扰着我们,让我们的migratet举步维艰,如何利用约束本身的属性来处理这些问题呢?本文详细介绍了约束的四对属性: Deferrable/not deferrable, Deferred/immediate, enalbe/disable, validate/novalidate,以及如
- Gradle入门教程
dengkane
gradle
一、寻找gradle的历程
一开始的时候,我们只有一个工程,所有要用到的jar包都放到工程目录下面,时间长了,工程越来越大,使用到的jar包也越来越多,难以理解jar之间的依赖关系。再后来我们把旧的工程拆分到不同的工程里,靠ide来管理工程之间的依赖关系,各工程下的jar包依赖是杂乱的。一段时间后,我们发现用ide来管理项程很不方便,比如不方便脱离ide自动构建,于是我们写自己的ant脚本。再后
- C语言简单循环示例
dcj3sjt126com
c
# include <stdio.h>
int main(void)
{
int i;
int count = 0;
int sum = 0;
float avg;
for (i=1; i<=100; i++)
{
if (i%2==0)
{
count++;
sum += i;
}
}
avg
- presentModalViewController 的动画效果
dcj3sjt126com
controller
系统自带(四种效果):
presentModalViewController模态的动画效果设置:
[cpp]
view plain
copy
UIViewController *detailViewController = [[UIViewController al
- java 二分查找
shuizhaosi888
二分查找java二分查找
需求:在排好顺序的一串数字中,找到数字T
一般解法:从左到右扫描数据,其运行花费线性时间O(N)。然而这个算法并没有用到该表已经排序的事实。
/**
*
* @param array
* 顺序数组
* @param t
* 要查找对象
* @return
*/
public stati
- Spring Security(07)——缓存UserDetails
234390216
ehcache缓存Spring Security
Spring Security提供了一个实现了可以缓存UserDetails的UserDetailsService实现类,CachingUserDetailsService。该类的构造接收一个用于真正加载UserDetails的UserDetailsService实现类。当需要加载UserDetails时,其首先会从缓存中获取,如果缓存中没
- Dozer 深层次复制
jayluns
VOmavenpo
最近在做项目上遇到了一些小问题,因为架构在做设计的时候web前段展示用到了vo层,而在后台进行与数据库层操作的时候用到的是Po层。这样在业务层返回vo到控制层,每一次都需要从po-->转化到vo层,用到BeanUtils.copyProperties(source, target)只能复制简单的属性,因为实体类都配置了hibernate那些关联关系,所以它满足不了现在的需求,但后发现还有个很
- CSS规范整理(摘自懒人图库)
a409435341
htmlUIcss浏览器
刚没事闲着在网上瞎逛,找了一篇CSS规范整理,粗略看了一下后还蛮有一定的道理,并自问是否有这样的规范,这也是初入前端开发的人一个很好的规范吧。
一、文件规范
1、文件均归档至约定的目录中。
具体要求通过豆瓣的CSS规范进行讲解:
所有的CSS分为两大类:通用类和业务类。通用的CSS文件,放在如下目录中:
基本样式库 /css/core
- C++动态链接库创建与使用
你不认识的休道人
C++dll
一、创建动态链接库
1.新建工程test中选择”MFC [dll]”dll类型选择第二项"Regular DLL With MFC shared linked",完成
2.在test.h中添加
extern “C” 返回类型 _declspec(dllexport)函数名(参数列表);
3.在test.cpp中最后写
extern “C” 返回类型 _decls
- Android代码混淆之ProGuard
rensanning
ProGuard
Android应用的Java代码,通过反编译apk文件(dex2jar、apktool)很容易得到源代码,所以在release版本的apk中一定要混淆一下一些关键的Java源码。
ProGuard是一个开源的Java代码混淆器(obfuscation)。ADT r8开始它被默认集成到了Android SDK中。
官网:
http://proguard.sourceforge.net/
- 程序员在编程中遇到的奇葩弱智问题
tomcat_oracle
jquery编程ide
现在收集一下:
排名不分先后,按照发言顺序来的。
1、Jquery插件一个通用函数一直报错,尤其是很明显是存在的函数,很有可能就是你没有引入jquery。。。或者版本不对
2、调试半天没变化:不在同一个文件中调试。这个很可怕,我们很多时候会备份好几个项目,改完发现改错了。有个群友说的好: 在汤匙
- 解决maven-dependency-plugin (goals "copy-dependencies","unpack") is not supported
xp9802
dependency
解决办法:在plugins之前添加如下pluginManagement,二者前后顺序如下:
[html]
view plain
copy
<build>
<pluginManagement
 ATACseq
ATACseq
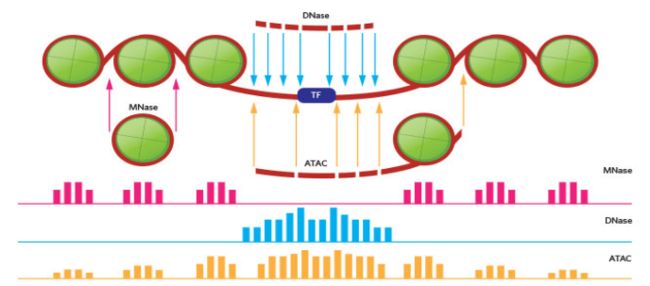 ATACseq, MNaseseq and DNaseseq
ATACseq, MNaseseq and DNaseseq