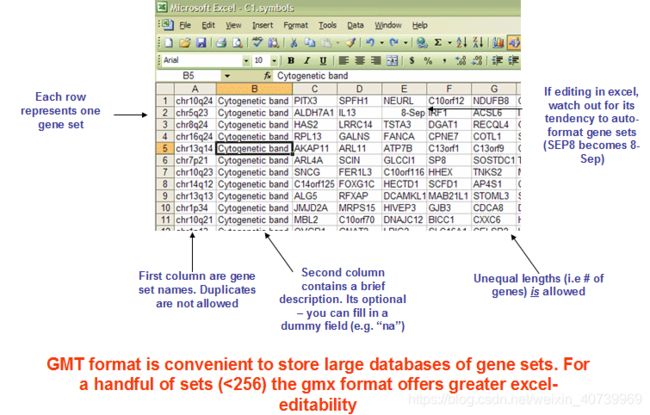
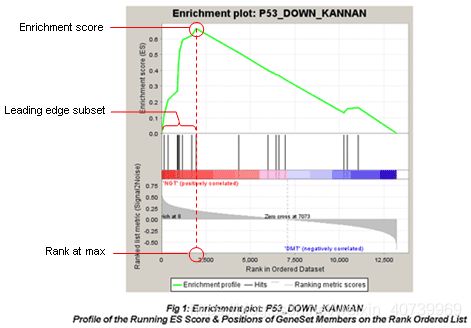
- 最新1区9+非肿瘤纯生信,逻辑清晰易懂,机器学习筛选关键基因的纯生信也可以发高水平期刊,抓紧上车!
生信小课堂
影响因子:9.186关于非肿瘤生信,我们也解读过很多,主要有以下类型1单个疾病WGCNA+PPI分析筛选hub基因2单个疾病结合免疫浸润,热点基因集,机器学习算法等。3两种相关疾病联合分析,包括非肿瘤结合非肿瘤,非肿瘤结合肿瘤或者非肿瘤结合泛癌分析4基于分型的非肿瘤生信分析5单细胞结合普通转录组生信分析目前非肿瘤生信发文的门槛较低,欢迎大家!研究概述:本研究首先使用R语言在三个基因表达数据集中找到
- 学生信息管理系统的VFP数据库设计与实现
溪水边小屋
本文还有配套的精品资源,点击获取简介:《学生管理系统vfp数据库》是一个基于VisualFoxPro(VFP)的学生信息管理软件,旨在帮助教育机构记录、管理学生数据并提供分析功能。该系统包括数据库设计、用户界面设计、数据操作、事务处理、报表统计、安全性管理、程序架构及代码优化等核心功能。学生管理系统是VFP数据库开发的学习和实践平台,适用于初学者。1.VisualFoxPro数据库开发基础Visu
- Tableau日常分析小技巧(2):数值中空值处理
Tableau日常小技巧
在日常分析中,我们常遇到数据源度量字段中有空值,那么,遇到这种情况我们如何在Tableau中做数据处理呢?数据源比较简单,如下图所示:将数据源导入TableauDesktop中,同时将类别放入‘行功能’,将销售额放入标记框文本中如图所示:表格中出现的空值是我们数据源中的缺失值,有两种方法可以处理缺失值方法一:使用zn()函数zn()函数表达式为zn(expression)表示如果表达式不为null
- leetcode 搜索二维矩阵 II python 四分法
DaydayHoliday
利用矩阵左上角元素总是最小,右下角总是最大的特性,将矩阵分成四部分,分别递归。请各位大佬多多提意见。classSolution(object):defsearchMatrix(self,matrix,target):""":typematrix:List[List[int]]:typetarget:int:rtype:bool"""row_num=len(matrix)ifrow_num==0:r
- 2019.6.12
星之梦lyx
又是一个大热天,课间操散步继续,正所谓冬练三九夏练三伏,如果没有课间跑步,孩子们在室内待的时间太长,不能呼吸失败的新鲜空气,课间时间又长给老师的管理带来很大的麻烦,同样是跑步老师掌握好了节奏和时间不会出现其他问题。教育局领导,两次发来信息督促毕业班学生信息资料收集情况,并且对这项工作再次提出更高的要求说明追责的办法,此项工作难度很大,学校停掉某一老师的课,专门负责这项工作确保准确顺利。昨天对没有按
- 【证明】对极几何:本质矩阵内在性质
Powerful_QI
slam线性代数矩阵
--这是目录--1.本质矩阵内在性质表述2.预备知识2.1线性代数基础2.1.1奇异值与特征值的关系2.1.2矩阵加减单位阵后特征值的变化2.2引理:一个常用的矩阵变换3.证明1.本质矩阵内在性质表述 本质矩阵(EssentialMatrix)EEE是一个3阶方阵,满足E=t∧RE=t^{\land}RE=t∧R其中RRR为旋转矩阵,ttt为平移量,t∧t^{\land}t∧运算定义如下(参考了
- Spring Framework 7.020.Spring 表达式语言(SpEL)Spring Expression Language
程序员勇哥
Java全套教程SpringFramework7springmysql数据库javaspringboot
SpringFramework7.020.Spring表达式语言(SpEL)SpringExpressionLanguageSpring表达式语言(SpEL)简介表达式求值核心特性类表达式集合数组映射函数操作符类型构造函数变量函数模板表达式bean定义中的表达式基于注解的配置中的表达式SpEL编译器解析器配置自定义评估上下文Spring表达式语言(简称SpEL)是一种强大的表达式语言,支持在运行时
- 学习笔记(33):matplotlib绘制简单图表-绘制混淆矩阵热图
宁儿数据安全
#机器学习学习笔记matplotlib
学习笔记(33):matplotlib绘制简单图表-绘制混淆矩阵热图一、绘制混淆矩阵热图代码解析1.1、导入必要的库importmatplotlib.pyplotaspltfromsklearn.metricsimportconfusion_matriximportseabornassnsmatplotlib.pyplot:Python中最常用的绘图库,用于创建各种图表confusion_matr
- NumPy-@运算符详解
GG不是gg
numpynumpy
NumPy-@运算符详解一、@运算符的起源与设计目标1.从数学到代码:符号的统一2.设计目标二、@运算符的核心语法与运算规则1.基础用法:二维矩阵乘法2.一维向量的矩阵语义3.高维数组:批次矩阵运算4.广播机制:灵活的形状匹配三、@运算符与其他乘法方式的核心区别1.对比`np.dot()`2.对比元素级乘法`*`3.对比`np.matrix`的`*`运算符四、典型应用场景:从基础到高阶1.深度学习
- 在生信分析中,处理vcf 比较好用的python包推荐
在生物信息学分析中,处理VCF(VariantCallFormat)文件的Python包有很多,以下是一些常用且好用的Python包,适合不同的分析需求:PyVCF(推荐)简介:PyVCF是一个专门为解析和操作VCF文件设计的Python库,支持读取、过滤和修改VCF文件。优点:简单易用,API直观。支持VCF4.0及以上版本。可以轻松访问变体的信息(如染色体、位置、参考碱基、变异碱基等)。安装:
- matlab计算转子系统的固有频率、振型、不平衡响应
可以计算转子系统的固有频率、振型、不平衡响应MatrixRiccati/code/Dichotomy_1(2).m,2210MatrixRiccati/code/Dichotomy_1.m,2210MatrixRiccati/code/RiccatiSY_1.m,2756MatrixRiccati/code/Trans1x(2).m,451MatrixRiccati/code/Trans1x.m,
- 力扣-73题 矩阵置零(C++)
JIngles123
#中等题
题目链接:https://leetcode-cn.com/problems/set-matrix-zeroes/题目如下:classSolution{public:voidsetZeroes(vector>&matrix){introw=matrix.size();intcol=matrix[0].size();vectorpos;//x0,y0,x1,y1,x2,y2...//通过一维数组的方式
- 力扣---矩阵置零
53488736abcdefg
leetcode矩阵算法
给定一个mxn的矩阵,如果一个元素为0,则将其所在行和列的所有元素都设为0。请使用原地算法。示例1:输入:matrix=[[1,1,1],[1,0,1],[1,1,1]]输出:[[1,0,1],[0,0,0],[1,0,1]]示例2:
- Python综合应用学生管理系统
主要是复习使用,希望大佬提意见整体结构与核心数据结构importosimportsysstudents=[]上述代码引入了os和sys模块,os模块用于处理文件和目录相关操作,sys模块提供了对Python解释器相关变量和函数的访问。students列表作为核心数据结构,用于存储所有学生的信息,后续对学生信息的增删改查操作都围绕它展开。菜单功能实现defmenu():"""显示程序菜单"""pri
- 云原生信息提取系统:容器化流程与CI_CD集成实践
一、问题引出:自动化信息获取为何难以工程化?在实际开发中,我们经常需要对互联网页面进行结构解析与内容提取,但这些任务常常陷入以下困境:本地测试没问题,一旦部署到线上环境便频繁出错;环境配置不一致导致执行失败;内容接口更新频繁,人工维护成本高;无法做到自动更新与持续运行;对接口访问策略缺乏灵活适配手段。这说明,仅靠“能运行的脚本”远远不够,信息提取任务也需要标准化的开发、测试与交付机制。二、真实挑战
- Magma代数软件利用KroneckerProduct扩展矩阵
黎玥烟
算法MAGMA矩阵
Magma代数软件代码//定义二元域F2:=GF(2);F3:=GF(3);v1:=[1,0,0,0,0,0,0,0,0,0,0];v2:=[0,1,0,0,0,0,0,0,0,1,0];v3:=[0,0,1,0,0,1,0,0,1,0,0];v4:=[0,0,0,1,0,1,0,1,0,0,0];v5:=[0,0,0,0,1,0,1,0,0,0,0];G1:=Matrix(F2,[ v1,v2
- java组件化设计_构建之路—谈谈组件化后端构建和实现
前言这一篇文章,准备了很久,构思了很久,草稿了很久。从个人编程至今,历经了C,C++,Java,到现如今的NodeJS。也后端到前端,再回到后端。更从学校里的学生信息管理系统到大型商业系统构建,是的,我曾一直以为编程也就是如此了,由瀑布模型,敏捷开发,设计模式等等组成的软件工程大致就是如此了。相信可能很多人也会有和我类似的想法,是否也都曾迷茫过?幸运的是,伴随着对前端的接触和深入,云雾散开。前端组
- 329. 矩阵中的最长递增路径C语言
给定一个mxn整数矩阵matrix,找出其中最长递增路径的长度。对于每个单元格,你可以往上,下,左,右四个方向移动。你不能在对角线方向上移动或移动到边界外(即不允许环绕)。来源:力扣(LeetCode)链接:https://leetcode-cn.com/problems/longest-increasing-path-in-a-matrix著作权归领扣网络所有。商业转载请联系官方授权,非商业转载
- 力扣 329. 矩阵中的最长递增路径
乔碧萝·乔斯达
leetcode矩阵算法
跳转至矩阵中的最长递增路径https://leetcode-cn.com/problems/longest-increasing-path-in-a-matrix/题目给定一个mxn整数矩阵matrix,找出其中最长递增路径的长度。对于每个单元格,你可以往上,下,左,右四个方向移动。你不能在对角线方向上移动或移动到边界外(即不允许环绕)。示例1:输入:matrix=[[9,9,4],[6,6,8]
- dp力扣 329. 矩阵中的最长递增路径
329.矩阵中的最长递增路径题目:链接https://leetcode.cn/problems/longest-increasing-path-in-a-matrix/代码:classSolution{public:structnode{inti;intj;intv;};staticboolcmp(nodex,nodey){returnx.vver;intlongestIncreasingPath
- [算法题解详细]DFS解力扣329矩阵中的最长递增路径
2401_84092508
程序员深度优先算法leetcode
输入:matrix=[[3,4,5],[3,2,6],[2,2,1]]输出:4解释:最长递增路径是[3,4,5,6]。注意不允许在对角线方向上移动。示例3输入:matrix=[[1]]输出:1提示m==matrix.lengthn==matrix[i].length1<=m,n<=2000<=matrix[i][j]<=2^31-1思路刚看到这题的时候我以为这题和岛屿最大面积这题差不多,但是提交了
- 03 数据可视化的世界非常广阔,除了已提到的类型,还有许多更细分或前沿的可视化形式。
晨曦543210
信息可视化人工智能
十五、机器学习与数据科学专用图表特征重要性图(FeatureImportancePlot)用途:展示机器学习模型中各特征对预测结果的贡献度。示例:随机森林模型中影响房价预测的关键因素。混淆矩阵热力图(ConfusionMatrixHeatmap)用途:分类模型性能评估,显示预测结果与真实标签的对比。示例:疾病诊断模型的真阳性/假阳性分布。学习曲线(LearningCurve)用途:分析模型训练过程
- 剑指 Offer 04. 二维数组中的查找
菜菜今天学习了吗
leetcode刷题leetcode算法数据结构
在一个n*m的二维数组中,每一行都按照从左到右递增的顺序排序,每一列都按照从上到下递增的顺序排序。请完成一个高效的函数,输入这样的一个二维数组和一个整数,判断数组中是否含有该整数。示例:现有矩阵matrix如下:[[1,4,7,11,15],[2,5,8,12,19],[3,6,9,16,22],[10,13,14,17,24],[18,21,23,26,30]]给定target=5,返回true
- 面试150 矩阵置0
Alfred king
面试150题目矩阵线性代数leetcode面试数组
思路我们使用两个标记集合,分别记录当矩阵的元素为0的时候的横、纵坐标。然后在对矩阵元素进行遍历,如果所在行或者所在列的索引在集合中,对应的矩阵元素修改为0即可```classSolution:defsetZeroes(self,matrix:List[List[int]])->None:"""Donotreturnanything,modifymatrixin-placeinstead."""ro
- C# 表达式语法详解
code_shenbing
C#c#开发语言
C#表达式语法详解C#表达式(Expression)是C#语言中最重要的组成部分之一,它用于计算值、执行操作或产生副作用。本文将全面深入地介绍C#中各种表达式的语法、用法和特性。一、表达式基础1.1表达式的定义表达式是由操作数、运算符和分隔符组成的序列,用于计算值或执行操作。表达式可以简单到一个字面量,也可以复杂到包含多个子表达式。1.2表达式的类型C#中的表达式可以分为以下几类:常量表达式:计算
- C# 集合表达式和展开运算符 (..) 详解
卷纸要用清风的
C#c#windows开发语言
集合表达式(`CollectionExpressions`)基本语法支持的集合类型展开运算符(`..`)基本用法实际应用示例创建新集合合并集合与现有API结合性能考虑高级用法多维集合自定义集合注意事项与传统方式的比较总结集合表达式(CollectionExpressions)C#12引入了集合表达式,提供了一种更简洁的方式来创建和初始化集合。基本语法//创建数组int[]array=[1,2,3]
- 如何记住js的正则表达式
HebyH_
javascript正则表达式数据库
正则表达式(RegularExpressions)是处理字符串的强大工具,但确实需要一些记忆和练习才能掌握。以下是一些帮助你记忆JavaScript正则表达式的方法和常用模式:1.基础结构记忆法记住正则表达式的基本结构:/pattern/flags-斜杠包围模式,后面可跟标志例如:/hello/gi-匹配"hello",全局且不区分大小写2.常用元字符记忆口诀"点星加问,花括号量".匹配任意单个字
- 正则表达式
虎皮辣椒小怪兽
Linux正则表达式
文章目录一、什么是正则表达式二、第一类正则三、第二类正则一、什么是正则表达式正则表达式(RegularExpression)是用于匹配字符串模式的工具。它可以高效地实现字符串的搜索、替换、验证等操作二、第一类正则元字符:指那些在正则表达式中具有特殊意义的专用字符,如:点(.)星(*)问号(?)等。前导字符:即位于元字符前面的字符abc*或aooo.1、.任意单个字符,除了换行符[root@loca
- LeetCode Hot 100 矩阵置零
源
leetcode矩阵算法
给定一个mxn的矩阵,如果一个元素为0,则将其所在行和列的所有元素都设为0。请使用原地算法。示例1:输入:matrix=[[1,1,1],[1,0,1],[1,1,1]]输出:[[1,0,1],[0,0,0],[1,0,1]]示例2:输入:matrix=[[0,1,2,0],[3,4,5,2],[1,3,1,5]]输出:[[0,0,0,0],[0,4,5,0],[0,3,1,0]]提示:m==ma
- LeetCode Hot 100 螺旋矩阵
给你一个m行n列的矩阵matrix,请按照顺时针螺旋顺序,返回矩阵中的所有元素。示例1:输入:matrix=[[1,2,3],[4,5,6],[7,8,9]]输出:[1,2,3,6,9,8,7,4,5]示例2:输入:matrix=[[1,2,3,4],[5,6,7,8],[9,10,11,12]]输出:[1,2,3,4,8,12,11,10,9,5,6,7]提示:m==matrix.lengthn
- xml解析
小猪猪08
xml
1、DOM解析的步奏
准备工作:
1.创建DocumentBuilderFactory的对象
2.创建DocumentBuilder对象
3.通过DocumentBuilder对象的parse(String fileName)方法解析xml文件
4.通过Document的getElem
- 每个开发人员都需要了解的一个SQL技巧
brotherlamp
linuxlinux视频linux教程linux自学linux资料
对于数据过滤而言CHECK约束已经算是相当不错了。然而它仍存在一些缺陷,比如说它们是应用到表上面的,但有的时候你可能希望指定一条约束,而它只在特定条件下才生效。
使用SQL标准的WITH CHECK OPTION子句就能完成这点,至少Oracle和SQL Server都实现了这个功能。下面是实现方式:
CREATE TABLE books (
id &
- Quartz——CronTrigger触发器
eksliang
quartzCronTrigger
转载请出自出处:http://eksliang.iteye.com/blog/2208295 一.概述
CronTrigger 能够提供比 SimpleTrigger 更有具体实际意义的调度方案,调度规则基于 Cron 表达式,CronTrigger 支持日历相关的重复时间间隔(比如每月第一个周一执行),而不是简单的周期时间间隔。 二.Cron表达式介绍 1)Cron表达式规则表
Quartz
- Informatica基础
18289753290
InformaticaMonitormanagerworkflowDesigner
1.
1)PowerCenter Designer:设计开发环境,定义源及目标数据结构;设计转换规则,生成ETL映射。
2)Workflow Manager:合理地实现复杂的ETL工作流,基于时间,事件的作业调度
3)Workflow Monitor:监控Workflow和Session运行情况,生成日志和报告
4)Repository Manager:
- linux下为程序创建启动和关闭的的sh文件,scrapyd为例
酷的飞上天空
scrapy
对于一些未提供service管理的程序 每次启动和关闭都要加上全部路径,想到可以做一个简单的启动和关闭控制的文件
下面以scrapy启动server为例,文件名为run.sh:
#端口号,根据此端口号确定PID
PORT=6800
#启动命令所在目录
HOME='/home/jmscra/scrapy/'
#查询出监听了PORT端口
- 人--自私与无私
永夜-极光
今天上毛概课,老师提出一个问题--人是自私的还是无私的,根源是什么?
从客观的角度来看,人有自私的行为,也有无私的
- Ubuntu安装NS-3 环境脚本
随便小屋
ubuntu
将附件下载下来之后解压,将解压后的文件ns3environment.sh复制到下载目录下(其实放在哪里都可以,就是为了和我下面的命令相统一)。输入命令:
sudo ./ns3environment.sh >>result
这样系统就自动安装ns3的环境,运行的结果在result文件中,如果提示
com
- 创业的简单感受
aijuans
创业的简单感受
2009年11月9日我进入a公司实习,2012年4月26日,我离开a公司,开始自己的创业之旅。
今天是2012年5月30日,我忽然很想谈谈自己创业一个月的感受。
当初离开边锋时,我就对自己说:“自己选择的路,就是跪着也要把他走完”,我也做好了心理准备,准备迎接一次次的困难。我这次走出来,不管成败
- 如何经营自己的独立人脉
aoyouzi
如何经营自己的独立人脉
独立人脉不是父母、亲戚的人脉,而是自己主动投入构造的人脉圈。“放长线,钓大鱼”,先行投入才能产生后续产出。 现在几乎做所有的事情都需要人脉。以银行柜员为例,需要拉储户,而其本质就是社会人脉,就是社交!很多人都说,人脉我不行,因为我爸不行、我妈不行、我姨不行、我舅不行……我谁谁谁都不行,怎么能建立人脉?我这里说的人脉,是你的独立人脉。 以一个普通的银行柜员
- JSP基础
百合不是茶
jsp注释隐式对象
1,JSP语句的声明
<%! 声明 %> 声明:这个就是提供java代码声明变量、方法等的场所。
表达式 <%= 表达式 %> 这个相当于赋值,可以在页面上显示表达式的结果,
程序代码段/小型指令 <% 程序代码片段 %>
2,JSP的注释
<!-- -->
- web.xml之session-config、mime-mapping
bijian1013
javaweb.xmlservletsession-configmime-mapping
session-config
1.定义:
<session-config>
<session-timeout>20</session-timeout>
</session-config>
2.作用:用于定义整个WEB站点session的有效期限,单位是分钟。
mime-mapping
1.定义:
<mime-m
- 互联网开放平台(1)
Bill_chen
互联网qq新浪微博百度腾讯
现在各互联网公司都推出了自己的开放平台供用户创造自己的应用,互联网的开放技术欣欣向荣,自己总结如下:
1.淘宝开放平台(TOP)
网址:http://open.taobao.com/
依赖淘宝强大的电子商务数据,将淘宝内部业务数据作为API开放出去,同时将外部ISV的应用引入进来。
目前TOP的三条主线:
TOP访问网站:open.taobao.com
ISV后台:my.open.ta
- 【MongoDB学习笔记九】MongoDB索引
bit1129
mongodb
索引
可以在任意列上建立索引
索引的构造和使用与传统关系型数据库几乎一样,适用于Oracle的索引优化技巧也适用于Mongodb
使用索引可以加快查询,但同时会降低修改,插入等的性能
内嵌文档照样可以建立使用索引
测试数据
var p1 = {
"name":"Jack",
"age&q
- JDBC常用API之外的总结
白糖_
jdbc
做JAVA的人玩JDBC肯定已经很熟练了,像DriverManager、Connection、ResultSet、Statement这些基本类大家肯定很常用啦,我不赘述那些诸如注册JDBC驱动、创建连接、获取数据集的API了,在这我介绍一些写框架时常用的API,大家共同学习吧。
ResultSetMetaData获取ResultSet对象的元数据信息
- apache VelocityEngine使用记录
bozch
VelocityEngine
VelocityEngine是一个模板引擎,能够基于模板生成指定的文件代码。
使用方法如下:
VelocityEngine engine = new VelocityEngine();// 定义模板引擎
Properties properties = new Properties();// 模板引擎属
- 编程之美-快速找出故障机器
bylijinnan
编程之美
package beautyOfCoding;
import java.util.Arrays;
public class TheLostID {
/*编程之美
假设一个机器仅存储一个标号为ID的记录,假设机器总量在10亿以下且ID是小于10亿的整数,假设每份数据保存两个备份,这样就有两个机器存储了同样的数据。
1.假设在某个时间得到一个数据文件ID的列表,是
- 关于Java中redirect与forward的区别
chenbowen00
javaservlet
在Servlet中两种实现:
forward方式:request.getRequestDispatcher(“/somePage.jsp”).forward(request, response);
redirect方式:response.sendRedirect(“/somePage.jsp”);
forward是服务器内部重定向,程序收到请求后重新定向到另一个程序,客户机并不知
- [信号与系统]人体最关键的两个信号节点
comsci
系统
如果把人体看做是一个带生物磁场的导体,那么这个导体有两个很重要的节点,第一个在头部,中医的名称叫做 百汇穴, 另外一个节点在腰部,中医的名称叫做 命门
如果要保护自己的脑部磁场不受到外界有害信号的攻击,最简单的
- oracle 存储过程执行权限
daizj
oracle存储过程权限执行者调用者
在数据库系统中存储过程是必不可少的利器,存储过程是预先编译好的为实现一个复杂功能的一段Sql语句集合。它的优点我就不多说了,说一下我碰到的问题吧。我在项目开发的过程中需要用存储过程来实现一个功能,其中涉及到判断一张表是否已经建立,没有建立就由存储过程来建立这张表。
CREATE OR REPLACE PROCEDURE TestProc
IS
fla
- 为mysql数据库建立索引
dengkane
mysql性能索引
前些时候,一位颇高级的程序员居然问我什么叫做索引,令我感到十分的惊奇,我想这绝不会是沧海一粟,因为有成千上万的开发者(可能大部分是使用MySQL的)都没有受过有关数据库的正规培训,尽管他们都为客户做过一些开发,但却对如何为数据库建立适当的索引所知较少,因此我起了写一篇相关文章的念头。 最普通的情况,是为出现在where子句的字段建一个索引。为方便讲述,我们先建立一个如下的表。
- 学习C语言常见误区 如何看懂一个程序 如何掌握一个程序以及几个小题目示例
dcj3sjt126com
c算法
如果看懂一个程序,分三步
1、流程
2、每个语句的功能
3、试数
如何学习一些小算法的程序
尝试自己去编程解决它,大部分人都自己无法解决
如果解决不了就看答案
关键是把答案看懂,这个是要花很大的精力,也是我们学习的重点
看懂之后尝试自己去修改程序,并且知道修改之后程序的不同输出结果的含义
照着答案去敲
调试错误
- centos6.3安装php5.4报错
dcj3sjt126com
centos6
报错内容如下:
Resolving Dependencies
--> Running transaction check
---> Package php54w.x86_64 0:5.4.38-1.w6 will be installed
--> Processing Dependency: php54w-common(x86-64) = 5.4.38-1.w6 for
- JSONP请求
flyer0126
jsonp
使用jsonp不能发起POST请求。
It is not possible to make a JSONP POST request.
JSONP works by creating a <script> tag that executes Javascript from a different domain; it is not pos
- Spring Security(03)——核心类简介
234390216
Authentication
核心类简介
目录
1.1 Authentication
1.2 SecurityContextHolder
1.3 AuthenticationManager和AuthenticationProvider
1.3.1 &nb
- 在CentOS上部署JAVA服务
java--hhf
javajdkcentosJava服务
本文将介绍如何在CentOS上运行Java Web服务,其中将包括如何搭建JAVA运行环境、如何开启端口号、如何使得服务在命令执行窗口关闭后依旧运行
第一步:卸载旧Linux自带的JDK
①查看本机JDK版本
java -version
结果如下
java version "1.6.0"
- oracle、sqlserver、mysql常用函数对比[to_char、to_number、to_date]
ldzyz007
oraclemysqlSQL Server
oracle &n
- 记Protocol Oriented Programming in Swift of WWDC 2015
ningandjin
protocolWWDC 2015Swift2.0
其实最先朋友让我就这个题目写篇文章的时候,我是拒绝的,因为觉得苹果就是在炒冷饭, 把已经流行了数十年的OOP中的“面向接口编程”还拿来讲,看完整个Session之后呢,虽然还是觉得在炒冷饭,但是毕竟还是加了蛋的,有些东西还是值得说说的。
通常谈到面向接口编程,其主要作用是把系统��设计和具体实现分离开,让系统的每个部分都可以在不影响别的部分的情况下,改变自身的具体实现。接口的设计就反映了系统
- 搭建 CentOS 6 服务器(15) - Keepalived、HAProxy、LVS
rensanning
keepalived
(一)Keepalived
(1)安装
# cd /usr/local/src
# wget http://www.keepalived.org/software/keepalived-1.2.15.tar.gz
# tar zxvf keepalived-1.2.15.tar.gz
# cd keepalived-1.2.15
# ./configure
# make &a
- ORACLE数据库SCN和时间的互相转换
tomcat_oracle
oraclesql
SCN(System Change Number 简称 SCN)是当Oracle数据库更新后,由DBMS自动维护去累积递增的一个数字,可以理解成ORACLE数据库的时间戳,从ORACLE 10G开始,提供了函数可以实现SCN和时间进行相互转换;
用途:在进行数据库的还原和利用数据库的闪回功能时,进行SCN和时间的转换就变的非常必要了;
操作方法: 1、通过dbms_f
- Spring MVC 方法注解拦截器
xp9802
spring mvc
应用场景,在方法级别对本次调用进行鉴权,如api接口中有个用户唯一标示accessToken,对于有accessToken的每次请求可以在方法加一个拦截器,获得本次请求的用户,存放到request或者session域。
python中,之前在python flask中可以使用装饰器来对方法进行预处理,进行权限处理
先看一个实例,使用@access_required拦截:
?