- 设计模式系列(10):结构型模式 - 桥接模式(Bridge)
系列导读:在学习了接口适配后,我们来看如何处理抽象与实现的分离问题。桥接模式解决的是"多维度变化"的设计难题。解决什么问题:将抽象部分与实现部分分离,使它们都可以独立变化。避免在多个维度上变化时出现类爆炸问题。想象一下,你要设计一个图形绘制系统,既要支持不同的形状(圆形、矩形),又要支持不同的绘制方式(Windows绘制、Linux绘制)。如果用继承,你需要WindowsCircle、LinuxC
- 如何自定义R语言函数?参数中的省略号`...`有什么用?
「已注销」
python编程语言java人工智能c++
学习R未必要学习很多工具包,有时候根据自己的理解去自定义函数也是一个不错的选择。本篇推文主要介绍两方面的内容:在R语言中自定义函数的一般方法;函数参数中...的作用。在看函数的帮助文档时会发现许多函数的参数中都有...符号,它是表示被省略的参数吗?如果是,作者为什么会省略它?如果不是,那又表示什么含义呢?不久前,学堂君分享了自己编写的计算空间可达性的函数,详见推文:两步移动搜索法(2SFCA)计算
- 人间生存小故事
是泡沫呀
瞎聊经验分享程序人生笔记生活职场和发展
知道吗,实现财富自由以后,那才是生活而在人间,每天为了不让自己饿死,那叫生存我会一直更新,记录一个个生存的故事,看看人们是怎么生存的1.地铁乘务员站岗坐标:深圳,车公庙地铁站,23年5月那天我19点下班,走到了地铁站,当我下楼梯时,大概距离地铁那扇门还有20米的样子,我一眼就看见了他------地铁乘务员他穿着一套黑色的制服,挺着一个大大的肚子,在那个列车小屏幕下站着,身体稍微的向前倾斜,就他一个
- Logistic回归预测模型2:R语言实现模型的内部和外部验证
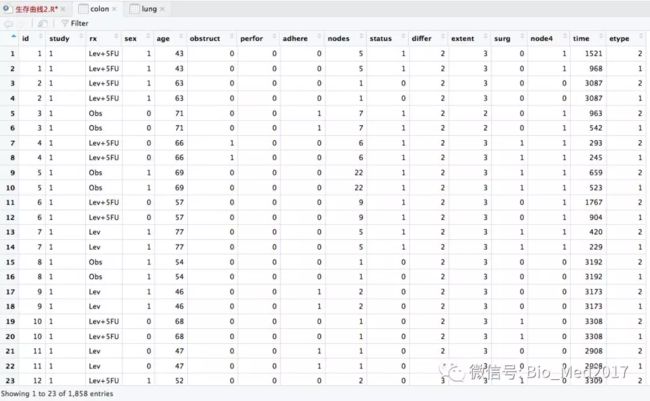
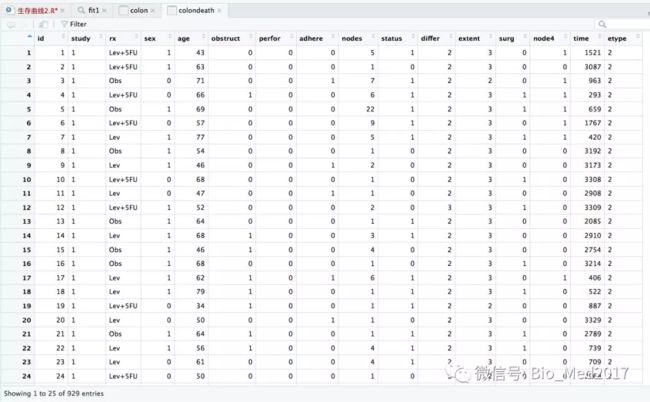
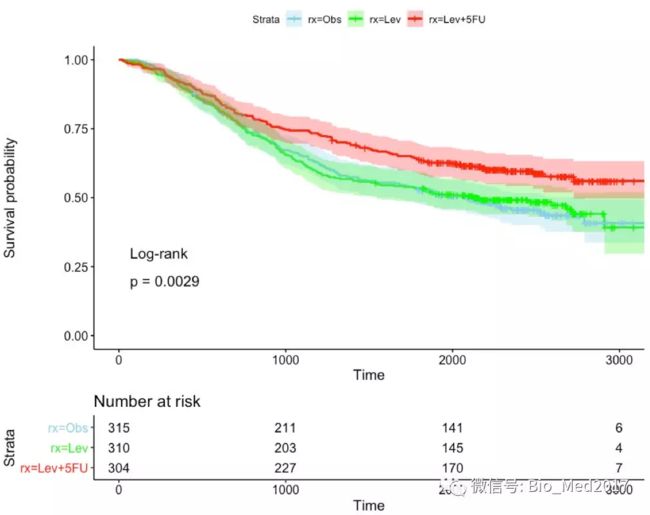
前面我们讲了logistic回归预测模型的建立,今天介绍的是模型的验证,可以在训练集和验证集中通过ROC曲线、校准曲线和决策曲线分别进行验证。1、原始数据原始数据分为训练集和验证集,其中训练集用于模型的构建和内部验证,验证集用于外部验证。两个数据集都包含5列,且列名相同。组别Group为因变量,1代表阳性结局,0代表阴性结局。自变量1和4为连续性变量,自变量2和3为二分类变量。2、安装所需要的R包
- R 列表:深入解析与高效应用
沐知全栈开发
开发语言
R列表:深入解析与高效应用引言在R语言中,列表(List)是一种非常重要的数据结构,它允许我们将不同类型的数据组合在一起。列表在数据分析和统计建模中扮演着至关重要的角色。本文将深入探讨R列表的概念、创建方法、操作技巧以及在实际应用中的高效使用。R列表概述定义R列表是一种可以包含多种数据类型的数据结构,如数值、字符、逻辑值、其他列表等。列表可以看作是一个容器,可以存储任意数量的元素。类型R列表分为两
- drawRect 触发时机
在iOS开发中,**UIView**的**drawRect:**方法(或其底层**CALayer**的绘制)的触发时机是由系统控制的,开发者不能直接调用这些方法。以下是触发视图绘制的完整机制:一、核心触发时机1.视图首次显示当视图被添加到视图层级时:[self.viewaddSubview:customView];//触发首次绘制2.显式标记需要重绘调用以下方法强制重绘://标记整个视图需要重绘[
- CALayer的异步处理
在iOS开发中,实现**CALayer**的异步处理是优化性能的关键技术,尤其对于复杂绘制或需要高性能渲染的场景。以下是完整实现方案:一、异步绘制核心架构设置异步绘制标志触发display创建异步任务执行绘制生成CGImage设置contents主线程CALayer实现displayLayer:方法全局队列CoreGraphics绘制主线程回调二、完整实现代码1.自定义异步图层//AsyncLay
- python炫酷烟花表白源代码,html代码烟花特效python
liuyifan0
pygamepython开发语言
大家好,小编来为大家解答以下问题,python绘制烟花特定爆炸效果,python炫酷烟花表白源代码,今天让我们一起来看看吧!代码实现:importpygameimportrandomimportmath#屏幕宽度SCREEN_WIDTH=1350SCREEN_HEIGHT=800#烟花颜色COLORS=[(255,0,0),(0,255,0),(0,0,255),(255,255,0),(255,
- 定制化APP:开启企业数字化转型新未来
知码客
程序员笔记运维定制化app
在当今快速发展的数字时代,企业的生存与发展不仅依赖于其传统的运营模式,更需要借助创新的技术手段来提升效率、优化服务并创造价值。而定制化的移动应用程序(简称“定制化APP”)正是实现这一目标的重要工具之一。通过量身定制的应用程序,企业能够更好地满足自身独特的业务需求,从而在激烈的市场竞争中脱颖而出。什么是定制化APP?定制化APP是指根据企业的特定需求设计和开发的移动应用软件。与市场上通用的应用程序
- OpenGL ES 纹理(7)
起司锅仔
OpenGLOpenGL安卓android
OpenGLES纹理(7)简述通过前面几章的学习,我们已经可以绘制渲染我们想要的逻辑图形了,但是如果我们想要渲染一张本地图片,这就需要纹理了。纹理其实是一个可以用于采样的数据集,比较典型的就是图片了,我们知道我们的片段着色器会对每一个像素都执行一次来计算,该像素应该渲染什么颜色,纹理就是一个数据集,比如想要渲染一个图片,我们就是用图片的所有像素信息作为总数据集,然后片段着色器计算的时候就根据像素坐
- 纯CSS实现有趣emoji切换开关
南城FE
前端CSS那些事南城前端专栏css前端
这是一个纯CSS创建的动画切换开关,它不仅能够在视觉上吸引用户,还能通过交互提供即时反馈。本文将解析源码的核心实现逻辑,这个项目的核心是使用CSS变量、3D变换和过渡效果来实现一个动态的、响应式的用户界面元素。关键技术点CSS变量:用于动态调整样式。3D变换:用于创建翻转动画效果。过渡效果:用于平滑地改变元素的样式。emoji:并不是真正的emoji而是通过CSS绘制。实现步骤1.HTML首先需要
- Android 自定义View 绘制一条颜色渐变,粗细渐变的线
nc_kai
笔记Android安卓
自定义View绘制一条颜色渐变,粗细渐变的线效果图如下:自定义View代码importandroid.annotation.SuppressLintimportandroid.content.Contextimportandroid.graphics.*importandroid.util.AttributeSetimportandroid.util.Logimportandroid.view.V
- 《支持向量机(SVM)在医疗领域的变革性应用》
CodeJourney.
支持向量机算法机器学习
在医疗科技日新月异的今天,先进的数据分析与机器学习技术正逐渐成为提升诊疗水平、助力医学研究的关键力量。支持向量机(SVM),凭借其独特的优势,在医疗这片复杂且对精准度要求极高的领域崭露头角,带来诸多令人瞩目的应用成果。一、疾病诊断:癌症早期筛查的“火眼金睛”癌症,作为全球健康的“头号杀手”,早期诊断对提升患者生存率意义非凡。在乳腺癌筛查领域,SVM发挥着重要作用。医疗科研人员收集大量乳腺组织的影像
- 前端相关性能优化笔记
星辰大海1412
笔记
1.打开速度怎么变快-首屏加载优化2.再次打开速度怎么变快-缓存优化了3.操作怎么才顺滑-渲染优化4.动画怎么保证流畅-长任务拆分2.1首屏加载指标细化:1.FP(FirstPaint首次绘制)2.FCP(FirstcontentfulPaint首次内容绘制),FP到FCP中间其实主要是SPA应用JS执行,太慢就会白屏时间太长3.FMP(FristMeaningfulPaint首次有效绘制),主要
- R 语言安装使用教程
小奇JAVA面试
安装使用教程r语言开发语言
一、R语言简介R是一种用于统计分析、数据挖掘和可视化的编程语言和环境。它在学术界和数据分析领域中广泛使用,拥有丰富的统计函数库和绘图功能。二、安装R语言2.1下载R安装包前往CRAN官网下载适合你操作系统的安装程序:官网地址:https://cran.r-project.org/2.2Windows安装下载.exe安装包;双击安装程序,按默认选项一路安装即可;安装完成后,可通过RGUI或命令行启动
- cesium-native+OpenGL开发笔记—渲染GIS球
坐标系转换OpenGL坐标系右手坐标系,X轴水平向右,Y轴竖直向上,Z轴指向屏幕外面。Y(绿色,朝上)^|||*---->X(红色,向右)//Z(蓝色,向前)(指向屏幕外)3DTiles坐标系右手坐标系,Z轴朝上Z(蓝色,朝上)^||/Y(绿色,朝屏幕内)|/*---->X(红色,朝右)glTF模型坐标系右手坐标系,Y轴朝上3DTiles和OpenGL坐标系上方向存在差异,实际绘制是在OpenGL
- 介绍Flutter
一、Flutter的核心优势:不止于跨平台高性能原生渲染自研引擎Skia:直接调用GPU绘制UI,绕过原生控件依赖,消除JavaScript桥接性能损耗,实现60fps流畅动画。三棵树渲染机制(Widget-Element-RenderObject):通过差异化更新最小化重绘范围,效率远超传统WebView方案。极速开发体验热重载(HotReload):代码修改后毫秒级生效,保留应用状态调试,开发
- Seaborn 教程
froginwe11
开发语言
Seaborn教程引言Seaborn是一个强大的Python数据可视化库,它建立在Matplotlib的基础上,专门用于统计图形的绘制。Seaborn提供了一系列的绘图功能,使得统计数据的可视化变得更加简单和直观。本文将为您提供一个全面的Seaborn教程,帮助您快速掌握其基本用法和高级技巧。安装与导入在开始之前,请确保您的Python环境中已经安装了Seaborn和Matplotlib。您可以使
- 新反洗钱法落地:代购系统“资金红线”与合规生存指南
反洗钱(AML)合规:代购系统如何规避资金风险?引言:代购系统的资金风险“暗流”代购系统作为跨境电商的重要纽带,连接着全球消费者与中国商品资源。然而,其“先收货款、后采购运输”的资金链模式,叠加跨境支付、虚拟货币、第三方平台等复杂场景,极易成为洗钱活动的“温床”。从现金走私到匿名支付,从虚假贸易到地下钱庄,代购系统面临的反洗钱(AML)合规挑战已从“隐性风险”升级为“生存红线”。本文将从政策法规、
- R语言学习笔记—删除对象
w1149033842
R语言
1.删除环境中的对象Arm(A)2.删除环境中的所有对象rm(list=is())3.删除除了A和B以外的所有对象allobj<-is()rm(list=allobj[which(allobj!="A"&allobj!="B")])
- R语言的游戏开发
柳婉晴
包罗万象golang开发语言后端
R语言在游戏开发中的应用随着科技的发展,游戏行业已经成为一个巨大的市场。虽然通常我们会认为游戏开发主要是使用C++、C#、JavaScript等语言,但实际上,R语言在游戏开发中也有其独特的应用,尤其是在数据分析和可视化方面。本文将探讨R语言在游戏开发中的应用,涵盖它的基础、游戏设计的复杂性、实际案例分析、以及未来的发展方向。一、R语言基础R语言是一种用于统计计算和数据分析的编程语言。它具有强大的
- R语言的软件开发工具
纪霁然
包罗万象golang开发语言后端
R语言的软件开发工具引言R语言因其强大的数据分析能力和丰富的统计包,自发布以来便广受欢迎。随着数据科学和分析的迅猛发展,R语言也逐渐成为数据分析、机器学习和统计建模领域的重要工具。为了更好地利用R语言进行软件开发,许多软件开发工具和环境应运而生。本文将深入探讨R语言的主要开发工具,帮助开发者更高效地进行数据处理和分析。1.R和RStudio基础R语言本身是一个用于统计计算和图形绘制的编程语言,而R
- R语言初学者爬虫简单模板
q56731523
r语言爬虫开发语言iphone
习惯使用python做爬虫的,反过来使用R语言可能有点不太习惯,正常来说R语言好不好学完全取决于你的学习背景以及任务复杂情况。对于入门学者来说,R语言使用rvest+httr组合,几行代码就能完成简单爬取(比Python的Scrapy简单得多),R语言数据处理优势明显,爬取后可直接用dplyr/tidyr清洗,小打小闹用R语言完全没问题,如果是企业级大型项目还是有限考虑python,综合成本还是p
- R语言开发记录,一
[email protected]
R语言r语言开发语言
1.清理环境rm(list=ls())gc()rm(list=ls())作用:删除当前R工作环境中所有的对象(变量、函数、数据框等)。解释:ls():列出当前环境中所有对象的名字。list=ls():将这些名字作为一个列表传给rm()函数。rm():移除这些对象。效果:相当于“清空内存”,让工作空间恢复到干净状态。gc()作用:手动触发垃圾回收(garbagecollection)。效果:释放R不
- Android阴影效果的艺术与实现:从入门到精通
大模型大数据攻城狮
android安卓动画canvaspaintandroid阴影安卓面试android面经
目录1.阴影的本质:为什么它对UI如此重要?2.深入MaterialDesign:理解Z轴与阴影层次3.兼容老版本:用Drawable实现阴影4.高级技巧:自定义OutlineProvider5.用Canvas绘制自定义阴影:解锁无限可能6.阴影性能优化:让丝滑体验飞起来7.JetpackCompose中的阴影实现:拥抱现代化8.动态阴影动画:打造炫酷交互效果9.RecyclerView中的阴影实
- 使用uniapp绘制一个折线图(uCharts)
苦夏木禾
uni-app
uCharts简介,这是官方介绍,上面有全部的示例,我这篇只是取一部分实现的需要引入u-charts.js,这个文件的代码我放在最后面,当然也可以官方Gitee下载效果图代码:importuChartsfrom'../../components/u-charts/u-charts.js';//引入js文件var_self;//用于全局使用thisvarcanvaLineA=null;//uChar
- 智能电动汽车 --- 车辆网关路由缓存
汽车电子实验室
电子电器架构—车载网关缓存ZEVonUDS-J1979OEM怎么掌握软件开发能力车载通信网络槪述HPC软件架构汽车
我是穿拖鞋的汉子,魔都中坚持长期主义的汽车电子工程师。老规矩,分享一段喜欢的文字,避免自己成为高知识低文化的工程师:简单,单纯,喜欢独处,独来独往,不易合同频过着接地气的生活,除了生存温饱问题之外,没有什么过多的欲望,表面看起来很高冷,内心热情,如果你身边有这样灵性的人,一定要好好珍惜他们眼中有神有光,干净,给人感觉很舒服,有超强的感知能力有形的无形的感知力很强,能感知人的内心变化喜欢独处,好静,
- 金融安全生命线:用AWS EventBridge和CloudTrail构建主动式入侵检测系统
运维开发王义杰
系统运维aws信息安全安全金融aws
今天,我们来聊一个硬核又极具价值的话题:如何为身处安全风暴中心的金融系统,构建一道坚不可摧的主动式入侵检测防线。在金融领域,安全不是一个选项,而是生存的基石。任何微小的疏忽都可能导致灾难性的资产损失。传统的防火墙和WAF固然重要,但面对日益复杂的内部威胁和APT攻击,我们需要更智能、更主动的监控手段。幸运的是,AWS为我们提供了两个强大的武器:CloudTrail和EventBridge。利用AW
- elkai库高效求解旅行商(TSP)问题(Pycharm23.01)
一九天虚
pythontsp问题旅行商问题
技术文档摘要简介本技术文档描述了一个基于elkai库实现的旅行商问题(TSP)求解与可视化工具,用于计算给定城市坐标的最优路径并展示结果。以下是核心功能与技术实现要点:1.核心功能TSP求解:通过elkai库高效求解城市坐标的最优访问顺序,最小化总路径成本。路径可视化:基于Matplotlib绘制路径图,动态标注起点、城市序号及路径走向。结果分析:输出路径总成本(目标值)及城市
- 从零到精通:Linux上的Conda环境详细教程
第一章:Conda简介Conda的定义Conda是一个开源的包管理系统和环境管理系统,可以在多个平台上安装、运行和更新软件包和依赖项。Conda最初是为Python和R语言的数据科学包创建的,但现在支持多种编程语言和工具。Conda的主要功能和优势包管理:Conda能够自动处理包的依赖关系,确保每个包所需的库和工具都被正确安装。它支持从各种渠道安装包,如CondaForge和Anaconda官方仓
- java数字签名三种方式
知了ing
javajdk
以下3钟数字签名都是基于jdk7的
1,RSA
String password="test";
// 1.初始化密钥
KeyPairGenerator keyPairGenerator = KeyPairGenerator.getInstance("RSA");
keyPairGenerator.initialize(51
- Hibernate学习笔记
caoyong
Hibernate
1>、Hibernate是数据访问层框架,是一个ORM(Object Relation Mapping)框架,作者为:Gavin King
2>、搭建Hibernate的开发环境
a>、添加jar包:
aa>、hibernatte开发包中/lib/required/所
- 设计模式之装饰器模式Decorator(结构型)
漂泊一剑客
Decorator
1. 概述
若你从事过面向对象开发,实现给一个类或对象增加行为,使用继承机制,这是所有面向对象语言的一个基本特性。如果已经存在的一个类缺少某些方法,或者须要给方法添加更多的功能(魅力),你也许会仅仅继承这个类来产生一个新类—这建立在额外的代码上。
- 读取磁盘文件txt,并输入String
一炮送你回车库
String
public static void main(String[] args) throws IOException {
String fileContent = readFileContent("d:/aaa.txt");
System.out.println(fileContent);
- js三级联动下拉框
3213213333332132
三级联动
//三级联动
省/直辖市<select id="province"></select>
市/省直辖<select id="city"></select>
县/区 <select id="area"></select>
- erlang之parse_transform编译选项的应用
616050468
parse_transform游戏服务器属性同步abstract_code
最近使用erlang重构了游戏服务器的所有代码,之前看过C++/lua写的服务器引擎代码,引擎实现了玩家属性自动同步给前端和增量更新玩家数据到数据库的功能,这也是现在很多游戏服务器的优化方向,在引擎层面去解决数据同步和数据持久化,数据发生变化了业务层不需要关心怎么去同步给前端。由于游戏过程中玩家每个业务中玩家数据更改的量其实是很少
- JAVA JSON的解析
darkranger
java
// {
// “Total”:“条数”,
// Code: 1,
//
// “PaymentItems”:[
// {
// “PaymentItemID”:”支款单ID”,
// “PaymentCode”:”支款单编号”,
// “PaymentTime”:”支款日期”,
// ”ContractNo”:”合同号”,
//
- POJ-1273-Drainage Ditches
aijuans
ACM_POJ
POJ-1273-Drainage Ditches
http://poj.org/problem?id=1273
基本的最大流,按LRJ的白书写的
#include<iostream>
#include<cstring>
#include<queue>
using namespace std;
#define INF 0x7fffffff
int ma
- 工作流Activiti5表的命名及含义
atongyeye
工作流Activiti
activiti5 - http://activiti.org/designer/update在线插件安装
activiti5一共23张表
Activiti的表都以ACT_开头。 第二部分是表示表的用途的两个字母标识。 用途也和服务的API对应。
ACT_RE_*: 'RE'表示repository。 这个前缀的表包含了流程定义和流程静态资源 (图片,规则,等等)。
A
- android的广播机制和广播的简单使用
百合不是茶
android广播机制广播的注册
Android广播机制简介 在Android中,有一些操作完成以后,会发送广播,比如说发出一条短信,或打出一个电话,如果某个程序接收了这个广播,就会做相应的处理。这个广播跟我们传统意义中的电台广播有些相似之处。之所以叫做广播,就是因为它只负责“说”而不管你“听不听”,也就是不管你接收方如何处理。另外,广播可以被不只一个应用程序所接收,当然也可能不被任何应
- Spring事务传播行为详解
bijian1013
javaspring事务传播行为
在service类前加上@Transactional,声明这个service所有方法需要事务管理。每一个业务方法开始时都会打开一个事务。
Spring默认情况下会对运行期例外(RunTimeException)进行事务回滚。这
- eidtplus operate
征客丶
eidtplus
开启列模式: Alt+C 鼠标选择 OR Alt+鼠标左键拖动
列模式替换或复制内容(多行):
右键-->格式-->填充所选内容-->选择相应操作
OR
Ctrl+Shift+V(复制多行数据,必须行数一致)
-------------------------------------------------------
- 【Kafka一】Kafka入门
bit1129
kafka
这篇文章来自Spark集成Kafka(http://bit1129.iteye.com/blog/2174765),这里把它单独取出来,作为Kafka的入门吧
下载Kafka
http://mirror.bit.edu.cn/apache/kafka/0.8.1.1/kafka_2.10-0.8.1.1.tgz
2.10表示Scala的版本,而0.8.1.1表示Kafka
- Spring 事务实现机制
BlueSkator
spring代理事务
Spring是以代理的方式实现对事务的管理。我们在Action中所使用的Service对象,其实是代理对象的实例,并不是我们所写的Service对象实例。既然是两个不同的对象,那为什么我们在Action中可以象使用Service对象一样的使用代理对象呢?为了说明问题,假设有个Service类叫AService,它的Spring事务代理类为AProxyService,AService实现了一个接口
- bootstrap源码学习与示例:bootstrap-dropdown(转帖)
BreakingBad
bootstrapdropdown
bootstrap-dropdown组件是个烂东西,我读后的整体感觉。
一个下拉开菜单的设计:
<ul class="nav pull-right">
<li id="fat-menu" class="dropdown">
- 读《研磨设计模式》-代码笔记-中介者模式-Mediator
bylijinnan
java设计模式
声明: 本文只为方便我个人查阅和理解,详细的分析以及源代码请移步 原作者的博客http://chjavach.iteye.com/
/*
* 中介者模式(Mediator):用一个中介对象来封装一系列的对象交互。
* 中介者使各对象不需要显式地相互引用,从而使其耦合松散,而且可以独立地改变它们之间的交互。
*
* 在我看来,Mediator模式是把多个对象(
- 常用代码记录
chenjunt3
UIExcelJ#
1、单据设置某行或某字段不能修改
//i是行号,"cash"是字段名称
getBillCardPanelWrapper().getBillCardPanel().getBillModel().setCellEditable(i, "cash", false);
//取得单据表体所有项用以上语句做循环就能设置整行了
getBillC
- 搜索引擎与工作流引擎
comsci
算法工作搜索引擎网络应用
最近在公司做和搜索有关的工作,(只是简单的应用开源工具集成到自己的产品中)工作流系统的进一步设计暂时放在一边了,偶然看到谷歌的研究员吴军写的数学之美系列中的搜索引擎与图论这篇文章中的介绍,我发现这样一个关系(仅仅是猜想)
-----搜索引擎和流程引擎的基础--都是图论,至少像在我在JWFD中引擎算法中用到的是自定义的广度优先
- oracle Health Monitor
daizj
oracleHealth Monitor
About Health Monitor
Beginning with Release 11g, Oracle Database includes a framework called Health Monitor for running diagnostic checks on the database.
About Health Monitor Checks
Health M
- JSON字符串转换为对象
dieslrae
javajson
作为前言,首先是要吐槽一下公司的脑残编译部署方式,web和core分开部署本来没什么问题,但是这丫居然不把json的包作为基础包而作为web的包,导致了core端不能使用,而且我们的core是可以当web来用的(不要在意这些细节),所以在core中处理json串就是个问题.没办法,跟编译那帮人也扯不清楚,只有自己写json的解析了.
- C语言学习八结构体,综合应用,学生管理系统
dcj3sjt126com
C语言
实现功能的代码:
# include <stdio.h>
# include <malloc.h>
struct Student
{
int age;
float score;
char name[100];
};
int main(void)
{
int len;
struct Student * pArr;
int i,
- vagrant学习笔记
dcj3sjt126com
vagrant
想了解多主机是如何定义和使用的, 所以又学习了一遍vagrant
1. vagrant virtualbox 下载安装
https://www.vagrantup.com/downloads.html
https://www.virtualbox.org/wiki/Downloads
查看安装在命令行输入vagrant
2.
- 14.性能优化-优化-软件配置优化
frank1234
软件配置性能优化
1.Tomcat线程池
修改tomcat的server.xml文件:
<Connector port="8080" protocol="HTTP/1.1" connectionTimeout="20000" redirectPort="8443" maxThreads="1200" m
- 一个不错的shell 脚本教程 入门级
HarborChung
linuxshell
一个不错的shell 脚本教程 入门级
建立一个脚本 Linux中有好多中不同的shell,但是通常我们使用bash (bourne again shell) 进行shell编程,因为bash是免费的并且很容易使用。所以在本文中笔者所提供的脚本都是使用bash(但是在大多数情况下,这些脚本同样可以在 bash的大姐,bourne shell中运行)。 如同其他语言一样
- Spring4新特性——核心容器的其他改进
jinnianshilongnian
spring动态代理spring4依赖注入
Spring4新特性——泛型限定式依赖注入
Spring4新特性——核心容器的其他改进
Spring4新特性——Web开发的增强
Spring4新特性——集成Bean Validation 1.1(JSR-349)到SpringMVC
Spring4新特性——Groovy Bean定义DSL
Spring4新特性——更好的Java泛型操作API
Spring4新
- Linux设置tomcat开机启动
liuxingguome
tomcatlinux开机自启动
执行命令sudo gedit /etc/init.d/tomcat6
然后把以下英文部分复制过去。(注意第一句#!/bin/sh如果不写,就不是一个shell文件。然后将对应的jdk和tomcat换成你自己的目录就行了。
#!/bin/bash
#
# /etc/rc.d/init.d/tomcat
# init script for tomcat precesses
- 第13章 Ajax进阶(下)
onestopweb
Ajax
index.html
<!DOCTYPE html PUBLIC "-//W3C//DTD XHTML 1.0 Transitional//EN" "http://www.w3.org/TR/xhtml1/DTD/xhtml1-transitional.dtd">
<html xmlns="http://www.w3.org/
- Troubleshooting Crystal Reports off BW
blueoxygen
BO
http://wiki.sdn.sap.com/wiki/display/BOBJ/Troubleshooting+Crystal+Reports+off+BW#TroubleshootingCrystalReportsoffBW-TracingBOE
Quite useful, especially this part:
SAP BW connectivity
For t
- Java开发熟手该当心的11个错误
tomcat_oracle
javajvm多线程单元测试
#1、不在属性文件或XML文件中外化配置属性。比如,没有把批处理使用的线程数设置成可在属性文件中配置。你的批处理程序无论在DEV环境中,还是UAT(用户验收
测试)环境中,都可以顺畅无阻地运行,但是一旦部署在PROD 上,把它作为多线程程序处理更大的数据集时,就会抛出IOException,原因可能是JDBC驱动版本不同,也可能是#2中讨论的问题。如果线程数目 可以在属性文件中配置,那么使它成为
- 正则表达式大全
yang852220741
html编程正则表达式
今天向大家分享正则表达式大全,它可以大提高你的工作效率
正则表达式也可以被当作是一门语言,当你学习一门新的编程语言的时候,他们是一个小的子语言。初看时觉得它没有任何的意义,但是很多时候,你不得不阅读一些教程,或文章来理解这些简单的描述模式。
一、校验数字的表达式
数字:^[0-9]*$
n位的数字:^\d{n}$
至少n位的数字:^\d{n,}$
m-n位的数字:^\d{m,n}$