概率编程库Pymc3案例之线性回归
参考:https://github.com/CamDavidsonPilon/Probabilistic-Programming-and-Bayesian-Methods-for-Hackers
1、模型假设
贝叶斯线性回归模型,假设参数具有正态分布(Normal)先验,要预测的具有正态分布的观测值 Y ,其期望 μ 是两个预测变量的线性组合, X1 和 X2 :
Y∼N(μ,σ2)
μ=α+β1X1+β2X2Y
其中 α 是截距, βi是变量 Xi的系数; σ 代表观察误差。
模型中的未知变量需要赋予先验分布,假设服从零均值的正态先验。其中,系数 α 、 βi的方差为100,选择半正态分布作为观测误差 σ的先验分布。
α∼N(0,100)
βi∼N(0,100)
σ∼|N(0,1)|
2、模拟数据生成
import numpy as np
import matplotlib.pyplot as plt
from mpl_toolkits.mplot3d import Axes3D
np.random.seed(123)
alpha=1
sigma=1
beta =[1, 2.5]
N=100
X1=np.random.randn(N)
X2=np.random.randn(N)
Y=alpha + beta[0]*X1 + beta[1]*X2 + np.random.randn(N)*sigma
%matplotlib inline
fig1,ax1 = plt.subplots(1, 2, figsize=(10,4));
ax1[0].scatter(X1, Y);ax1[0].set_xlabel('X1');ax1[0].set_ylabel('Y');
ax1[1].scatter(X2, Y);ax1[1].set_xlabel('X2');ax1[1].set_ylabel('Y');
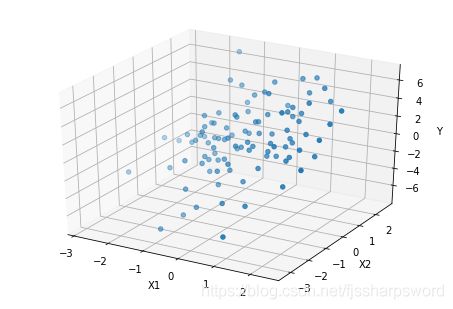
fig2 = plt.figure(2);
ax2 = Axes3D(fig2);
ax2.scatter(X1,X2,Y);
ax2.set_xlabel('X1');
ax2.set_ylabel('X2');
ax2.set_zlabel('Y');2、利用pymc3定义模型
import pymc3 as pm
with pm.Model() as basic_model:
alpha=pm.Normal('alpha',mu=0,sd=10)
beta=pm.Normal('beta',mu=0,sd=10,shape=2)
sigma=pm.HalfNormal('sigma',sd=1)
mu=alpha+beta[0]*X1+beta[1]*X2
Y_obs=pm.Normal('Y_obs',mu=mu,sd=sigma,observed=Y)定义了三个具有正态分布先验的随机性随机变量(stochastic random veriables)。
定义了一个确定性随机变量(deterministic random veriable),确定性指这个变量的值完全由右端值确定。
最后定义了 Y 的观测值,这是一个特殊的观测随机变量(observed stochastic),表示模型数据的可能性。通过 observed 参数来告诉这个变量其值是已经被观测到了的(就是 Y 变量),不会被拟合算法改变。可以用 numpy.ndarry 或 pandas.DataFrame 对象作为数据参数传入。
3、模拟拟合
3.1 MAP方法
使用最优化方法找到点估计,快速简单。PyMC3提供了 find_MAP 函数,返回参数的一个估计值(point)。
默认情况下,find_MAP 使用Broyden–Fletcher–Goldfarb–Shanno (BFGS) 算法进行最优化运算,找到对数后验分布的最大值。这里也可以指定 scipy.optimize 模块中的其他最优化算法完成寻优。
map_estimate = pm.find_MAP(model=basic_model)
from scipy import optimize
map_estimate2 = pm.find_MAP(model=basic_model,fmin=optimize.fmin_powell)
print(map_estimate)
print(map_estimate2)Optimization terminated successfully.
Current function value: 148.980478
Iterations: 6
Function evaluations: 269
{'sigma': array(0.96298715), 'sigma_log__': array(-0.03771521), 'alpha': array(0.90661753), 'beta': array([0.94850377, 2.52246124])}
{'sigma': array(0.96298742), 'sigma_log__': array(-0.03771493), 'alpha': array(0.90661033), 'beta': array([0.94849417, 2.5224695 ])}
值得注意的是,MAP估计不总是有效的,特别是在极端模型情况下。在高维后验中,可能出现某一出概率密度异常大,但整体概率很小的情况,在层次化模型中较为常见。
大多数寻找MAP极大值算法都找到局部最优解,那么这种算法这在差异非常大的多模态后验中会失效。
3.2 MCMC方法
虽然极大后验估计是一个简单快速的估计未知参数的办法,但是没有对不确定性进行估计是其缺陷。相反,比如MCMC这类基于采样的方法可以获得后验分布接近真实的采样值。
为了使用MCMC采样以获得后验分布的样本,PyMC3需要指定和特定MCMC算法相关的步进方法(采样方法),如Metropolis, Slice sampling, or the No-U-Turn Sampler (NUTS)。PyMC3中的 step_methods 子模块提供了如下采样器: NUTS, Metropolis, Slice, HamiltonianMC, and BinaryMetropolis。可以由PyMC3自动指定也可以手动指定。自动指定是根据模型中的变量类型决定的:
* 二值变量:指定 BinaryMetropolis
* 离散变量:指定 Metropolis
* 连续变量:指定 NUTS
手动指定优先,可覆盖自动指定。
PyMC3有许多基本采样算法,如自适应切片采样、自适应Metropolis-Hastings采样,但最厉害是的No-U-Turn采样算法(NUTS),特别是在具有大量连续型参数的模型中。NUTS基于对数概率密度的梯度,利用了高概率密度的区域信息,以获得比传统采样算法更快的收敛速度。PyMC3使用Theano的自动微分运算来进行后验分布的梯度计算。通过自整定步骤来自适应的设置Hamiltonian Monte Carlo(HMC)算法的可调参数。NUTS不可用于不可微分变量(离散变量)的采样,但是对于具有不可微分变量的模型中的可微分变量是可以使用的。
NUTS需要一个缩放矩阵作为参数,这个矩阵提供了分布的大致形状,使NUTS不至于在某些方向上的步长过大而在另外一些方向上的步长过小。设置有效的缩放矩阵有助于获得高效率的采样,特别是对于那些有很多未知的(未被观察的)随机型随机变量的模型或者具有高度非正态后验的模型。不好的缩放矩阵将导致采样速度很慢甚至完全停止。此外,在多数时候,采样的初始位置对于高效的采样也是很关键的。
幸运的是,PyMC3使用自动变分推理ADVI (auto-diff variational inference)来初始化NUTS算法,并在 step 参数没有被指定的情况下会自动指定一个合适的迭代方法(step,采样器)。
with basic_model:
#trace = pm.sample(2000)
step = pm.NUTS()#step = pm.Metropolis()
trace = pm.sample(2000,step=step)Multiprocess sampling (4 chains in 4 jobs)
NUTS: [sigma, beta, alpha]
Sampling 4 chains: 100%|██████████| 10000/10000 [00:03<00:00, 2997.90draws/s]print("alpha",trace['alpha'].shape)
print(trace['alpha'][0:5],"\n")
print("beta",trace['beta'].shape)
print(trace['beta'],"\n")
print("sigma",trace['sigma'].shape)
print(trace['sigma'])alpha (8000,)
[1.04278775 0.88323412 0.88755258 0.87381961 0.89942359]
beta (8000, 2)
[[1.01046211 2.55993421]
[1.00954145 2.54110235]
[0.91388241 2.45626273]
...
[1.16787685 2.60887027]
[0.7255497 2.42006215]
[1.00161371 2.75913019]]
sigma (8000,)
[0.91877597 1.17095769 0.87067159 ... 1.02761247 0.95970655 1.05418962]可以通过 step 参数指定特定的采样器(迭代器)来替换默认的迭代器NUTS。这里给 sigma 变量指定 Slice 采样器(step),那么其他两个变量( alpha 和 beta)的采样器会自动指定(NUTS)。
with basic_model:
# 用MAP获得初始点
start = pm.find_MAP(fmin=optimize.fmin_powell)
# 实例化采样器
step = pm.Slice(vars=[sigma])
# 对后验分布进行5000次采样
trace = pm.sample(5000, step=step,start=start)/home/fjs/.local/lib/python3.5/site-packages/pymc3/tuning/starting.py:61: UserWarning: find_MAP should not be used to initialize the NUTS sampler, simply call pymc3.sample() and it will automatically initialize NUTS in a better way.
warnings.warn('find_MAP should not be used to initialize the NUTS sampler, simply call pymc3.sample() and it will automatically initialize NUTS in a better way.')
/home/fjs/.local/lib/python3.5/site-packages/pymc3/tuning/starting.py:102: UserWarning: In future versions, set the optimization algorithm with a string. For example, use `method="L-BFGS-B"` instead of `fmin=sp.optimize.fmin_l_bfgs_b"`.
warnings.warn('In future versions, set the optimization algorithm with a string. '
logp = -149: 5%|▌ | 269/5000 [00:00<00:01, 3256.65it/s]
Optimization terminated successfully.
Current function value: 148.980478
Iterations: 6
Function evaluations: 269
Multiprocess sampling (4 chains in 4 jobs)
CompoundStep
>Slice: [sigma]
>NUTS: [beta, alpha]
Sampling 4 chains: 100%|██████████| 22000/22000 [00:08<00:00, 2581.19draws/s]4、后验分布分析
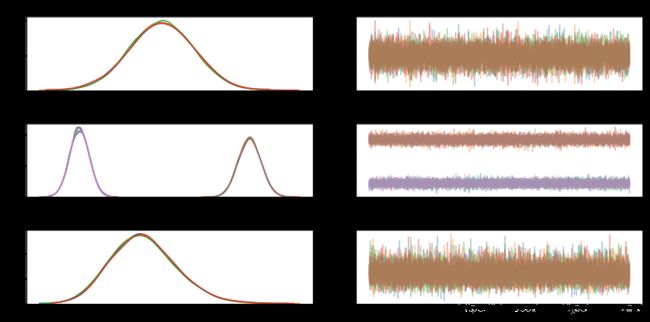
PyMC3提供了 traceplot 函数来绘制后验采样的趋势图。
pm.traceplot(trace);左侧是每个随机变量的边际后验的直方图,使用核密度估计进行了平滑处理。右侧是马尔可夫链采样值按顺序绘制。对于向量参数 beta会有两条后验分布直方图和后验采样值。
同时也提供蚊子形式的后验统计总结,使用summary函数获得。
pm.summary(trace)前面设置的参数如下
alpha=1
beta =[1, 2.5]
sigma=1这里通过后验估计可以看出平均估计值:
mean(alpha)=[0.906]
mean(beta)=[0.948,2.522]
mean(sigma)=[0.991]